本次为各位老师带来华中农业大学邓秀新教授团队在Plant Journal中发表的研究论文,题目为“Adventitious embryonic causal gene FhRWP?regulates multiple developmental phenotypes in citrus reproduction”,该文章利用ATAC-seq和转录组技术,探究了柑橘中无性繁殖现象——不定胚发生的机制。百迈客生物为该研究提供了ATAC-seq测序服务。

研究背景
植物的再生和发育是一个关键的过程,涉及从组织、器官、愈伤组织甚至具有多能性或多能性的单个细胞中重建整个植物,并通过复杂的调控网络进行细胞命运的转化,深入了解植物的再生和发育,对于设计提高作物再生效率的分子工具至关重要。
不定胚直接从获得胚性命运的珠心组织细胞亚群发育而来,作为有性生殖的替代品,在柑橘和芒果等少数植物中已有报道,因此,对不定胚胎发生的研究可以为植物再生和发育的遗传机制提供独特的视角;由于缺乏合适的遗传系统来探索潜在机制,我们对不定胚和再生之间关系的理解非常有限,在植物再生工程应用中,目前已有部分基因被鉴定并用于促进植物再生,从而克服了与物种相关的局限性,FhRWP的功能和不定胚的调节网络仍在很大程度上未被了解,已有研究提出,染色质重塑复合体亚基?被认为能够诱导FhRWP的高表达,该研究通过整合转录组与染色质开放图景数据阐明了FhRWP表达与其表观遗传调控之间的调控关系。
材料及方法
材料:单胚基因型和多胚基因型山橘胚珠、腋芽、幼叶及胚源性愈伤组织等;
方法:ATAC+转录组+重测序+激素检测等
研究结果
1.多胚山橘的开放性染色质
为了揭示来自珠粒细胞的外胚的重编程模式,作者采用ATAC-seq分析了多胚(PO)及单胚(MO)基因型山橘后胚的胚珠的全基因组染色质可及性,结果表明,PO特异性开放染色质区域(ACRs)基因参与了次级代谢过程、生长正调控、细胞分化和正向调控细胞生长。
先前的研究表明,一个显性基因FhRWP决定了与微型倒重复转座因子(MITE)插入相关的不定胚胎的启动,在PO基因型中FhRWP的启动子区中鉴定到了特异性ACR,而Mo基因型中不含ACR,该ACR与FhRWP启动子区域的MITE序列重叠,即MITE序列被FhARID1蛋白结合,这可能是染色质重塑复合体的一个亚基,这些结果表明,FhRWP是可及染色质的决定因素,参与不定胚胎发育,与MITE的插入有关。
山橘基因组中与组织再生和体细胞胚胎发生相关的hub基因,研究结果表明,与组织再生和体细胞胚胎发生相关的hub基因,有12个ACRs特异性转录因子在PO和Mo基因型柑橘品种之间存在差异表达,WUSCHEL(WUS)基因是干细胞维持的关键调控因子,在PO基因型柑橘中表达上调。FhKRP7kip相关蛋白(KRP)基因编码一种细胞周期蛋白依赖性激酶抑制剂(CKI),是细胞分裂的负调控因子。而FhKRP在PO基因型中下调了0.59倍。总的来说,分析显示,多胚胎基因型可能具有更大的染色质可及性区域,促进植物重编程通路相关基因来调控不定胚的形成。

2.FhRWP基因的基因编辑结果展示其在不定胚发生中的作用
FhRWP基因在胚囊中的表达是特异性和短暂的,可以从受精前7天开始追踪,直到后10天,作者采用RNAi方法构建了6个干扰系,发现FhRWP在6个干扰系中的表达量相比PO系显著降低,但显著高于Mo基因型,且FhRWP表达量降低后不定胚数量也都减少了,这些结果提示,受FhRWP控制的不定胚表型可能与基因表达的剂量效应有关。
作者之前的研究显示的杂合子插入MITE启动子区域和一个FhRWP的CDS序列区域SNP(C-G),导致这个基因的分裂成两个单倍型,M等位基因(MITE)和P等位基因(没有MITE)。根据Mo和PO腋芽的转录组结果,作者发现PO中RWP转录本高表达P等位基因,而Mo中M等位基因表达较小,于是作者构建了CRISPR/Cas9载体,以敲除FhRWP,结果表明,插入MITE可以通过促进含有MITE的P等位基因的表达,同时减少不插入MITE的M等位基因的表达,从而改变该基因的表达模式。虽然FhRWP在ko-47-1和ko-47-2中的FhRWP的表达下降到与Mo一致的水平,但P等位基因突变导致的过早终止导致了FhRWP功能的丧失,因此,ko-47-1和ko-47-2植株表现出新的表型,如生长迟缓和花芽分化失败。
此外,对对照和转基因株系的腋芽进行差异表达分析发现,这些基因在确定植物器官特性和植物器官形成等过程中存在明显的富集,与开花相关的FT/TFL1基因家族的表达也存在差异;此外,有研究表明CEN促进了芽的休眠作用,通过酵母单杂交,发现FhRWP直接调控FhCEN的启动子区域。
柑橘胚愈伤组织的诱导具有明显的基因型依赖性,作者在Mo基因型山橘中过表达FhRWP的P等位基因CDS,检测到GFP的植株胚胎愈伤组织增长迅速。qRT-PCR显示FhRWP表达高度上调,细胞分裂素、ABA和水杨酸激素水平有显著变化,而生长素和赤霉素水平则无显著性差异,FhRWP的过表达有助于Mo基因型山橘茎段上胚胎愈伤组织的形成。转录组结果显示,WUS和CLV1等再生途径相关的低丰度基因表达上调,在OE-FhRWP愈伤组织中,WUS与CLV1表达量增加,与激素分析结果一致,与ABA和细胞分裂素合成途径相关的基因,包括IPT、CKK、AHK、PYL的表达存在显著差异。

3.FhRWP在柑橘多种组织繁殖中的多效性
多项实验结果表明,FhRWP在协调细胞命运和启动植物再生和繁殖过程中起着关键作用,因此,该研究对腋芽MO/PO胚珠的表达数据进行了整合的转录组分析。差异基因在花器官发生和繁殖相关的生物过程显著富集,其中来自MADS和WOX等基因家族的转录因子,包括FhWUS和FhAGL6,均显著富集,在过表达的愈伤组织中,共鉴定出354个差异表达的转录因子,GO注释显示与胚胎后发育和再生相关的过程显著相关。值得注意的是,属于GRF和TALE等基因家族的转录因子,包括FhAHT1和FhGRF1,表现出显著的富集,这些基因已被广泛报道参与光形态建成、叶片发育等信号通路。
同时,作者在Mo和PO胚珠中发现了56个差异表达的转录因子,它们与分生组织维持和胚胎后发育相关的过程显著相关,其中,来自NAC、NAC等基因家族的转录因子,包括FhNAC等转录因子显著富集。此外,还发现了另一个与柑橘核细胞胚发育密切相关的转录因子FhC2H2,这些基因参与了伤口的愈合、再生和繁殖,研究结果表明,FhRWP可能是一个关键的调控枢纽,通过调节下游转录调控网络和影响各种组织来影响植物的再生。

思路发散
该研究从ATAC-seq入手,先从特异性及差异开放区域相关基因中筛选出来部分目的基因,再结合转录组基因表达以及大量基因编辑逐步完善FhRWP调节柑橘繁殖中的多效性,与直接从转录组入手筛选基因相比,初筛的基因范围可能会更小,更利于进一步锁定关键基因,为后续其他研究提供了新的思路。
]]>参考文献:
Song X, Wang N, Zhou Y, Tian X, Xie Z, Chai L, Wu X, Xu Q, Zhang F, Ye J, Deng X. Adventitious embryonic causal gene FhRWP regulates multiple developmental phenotypes in citrus reproduction. Plant J. 2024 Aug;119(3):1494-1507. doi: 10.1111/tpj.16870. Epub 2024 Jun 16.

英文标题:Haplotype‐resolved genome of a papeda provides insights into the geographical origin and evolution of Citrus
发表期刊:Journal of Integrative Plant Biology
影响因子:9.3
合作单位:西南大学柑桔研究所等
百迈客生物为该研究提供了基因组测序及组装等相关工作。
研究背景
柑橘是世界上种植最广泛的水果之一,目前在140多个国家和地区种植。虽然过去的二十年里柑橘植物的种群结构和遗传多样性已被调查,但由于其丰富的资源类型和杂交频繁,许多柑橘物种的起源和进化仍不清楚。野生柑橘物种和原始柑橘保存了丰富的遗传资源和遗传多样性,可用于阐明柑橘物种的起源和进化。2015年,在西双版纳发现一棵200多年的野生柑橘树大翼叶柑橘(DYC002),被认为是研究柑橘进化及苦味驯化的很好材料。
研究方法
DYC002单倍型基因组组装:PacBio HiFi 180×;llumina 75×;HIC 134×
群体进化研究:378份具有代表性的材料进行全基因组重测序分析;平均测序深度32.6×
DYC002转录组测序:幼叶、茎、花、小果和根(3个生物学重复)
研究结果
作者利用53.7G PacBio HiFi、22.6G illumina reads和40.1G Hi-Creads,首先组装出318.71 Mbp大小的contig版本基因组,contig N50为2.48 M,接着利用HIC数据将contig 挂载到染色体上,得到得到294 Mbp的基因组,BUSCO评估完整性大于98%,LTR组装指数(LAI)得分高达21.1,测序数据回比率为97.43%,进一步支持了组装的完整性。最后对DYC002基因组注释,共注释到34,652个蛋白编码基因和215,693个重复序列。重复序列多为LTR,尤其是Gypsy LTR和Copia LTR,占组装基因组的23.62%。比较基因组发现DYC002有191个基因家族正在快速进化。GO富集分析表明,这些快速进化的基因主要富集于萜烯合酶活性、倍半萜合酶活性、(4S)-柠檬烯合酶活性、(E)-柠檬烯合酶活性、葡萄糖苷酶活性和-葡萄糖苷酶活性等功能,表明DYC002在进化过程中香气和风味发生了显著变化。
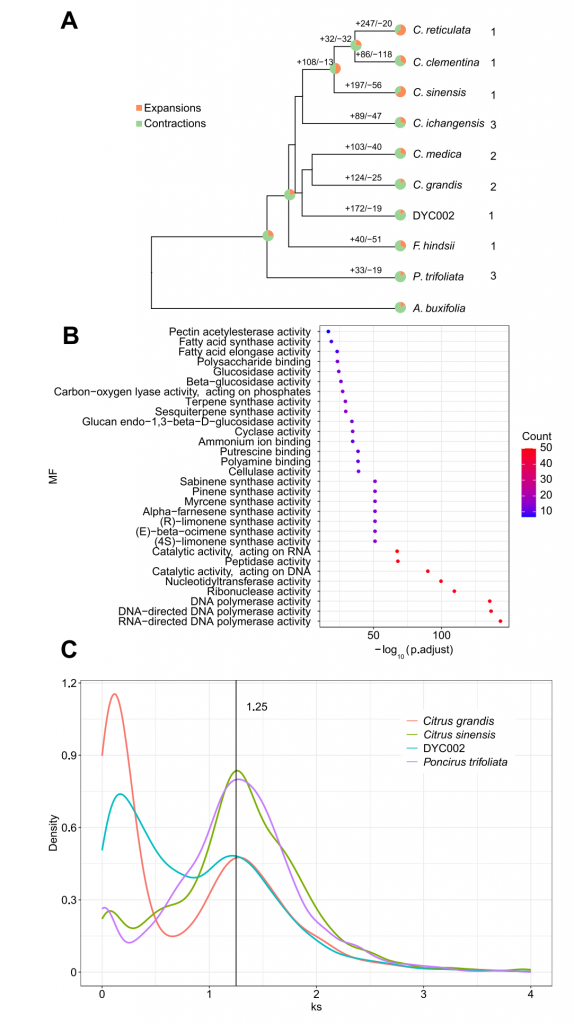
图1-比较基因组分析
利用CCS数据和HIC数据,作者组装出DYC002的两套单倍型基因组,长度分别为294和300 Mbp,注释的基因数量分别为28000和27785个;BUSCO完整度分别为97.39%和97.33%。通过比较分析,两单倍型基因组间存在175万个SNPs,303,686个Indels,转录组分析表明,两个单倍型中等位基因的表达高度一致。叶片中等位基因特异性表达基因(ASEGs)数量最高,而花中数量最低。在单倍型1和单倍型2的组装中分别发现了535个和499个单倍型特异性基因。
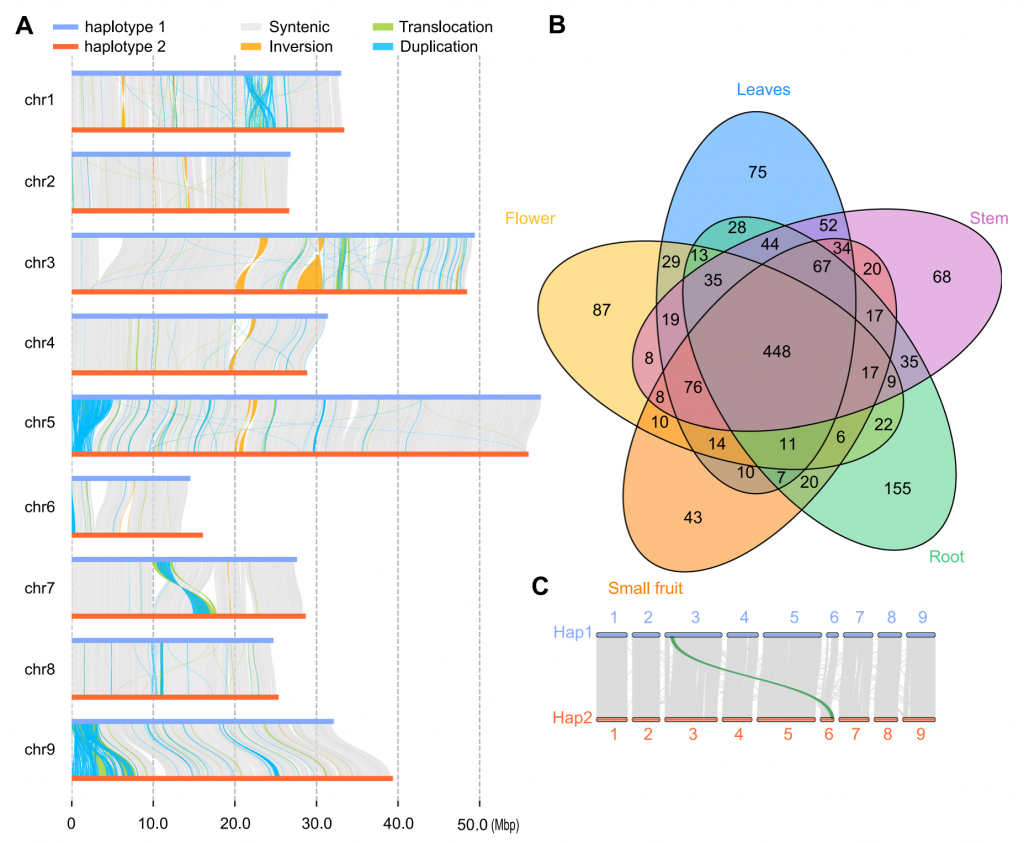
图2-单倍型基因组比较分析
为了说明柑橘物种的进化历史,作者从378份具有代表性的柑橘材料中获得了基因组重测序数据,利用核基因组SNPs进行的系统发育分析,除了莽山野柑,柑橘属可分为两个进化支,一支以宽皮柑橘、宜昌橙、香橙、甜橙等为代表,另一支包括大翼橙、澳指檬、澳沙檬、枸橼、红河大翼橙、柚、酸橙等。推测柑橘属植物从起源中心朝东南亚和中国东部两个方向进行演化和传播。选择性清除分析表明,苦味在柑橘驯化过程中具有较高的选择,共鉴定出672个选择性扫描区,一些参与类柠檬苦素和类黄酮生物合成的4-香豆酸-CoA连接酶、糖苷转移酶受到选择。
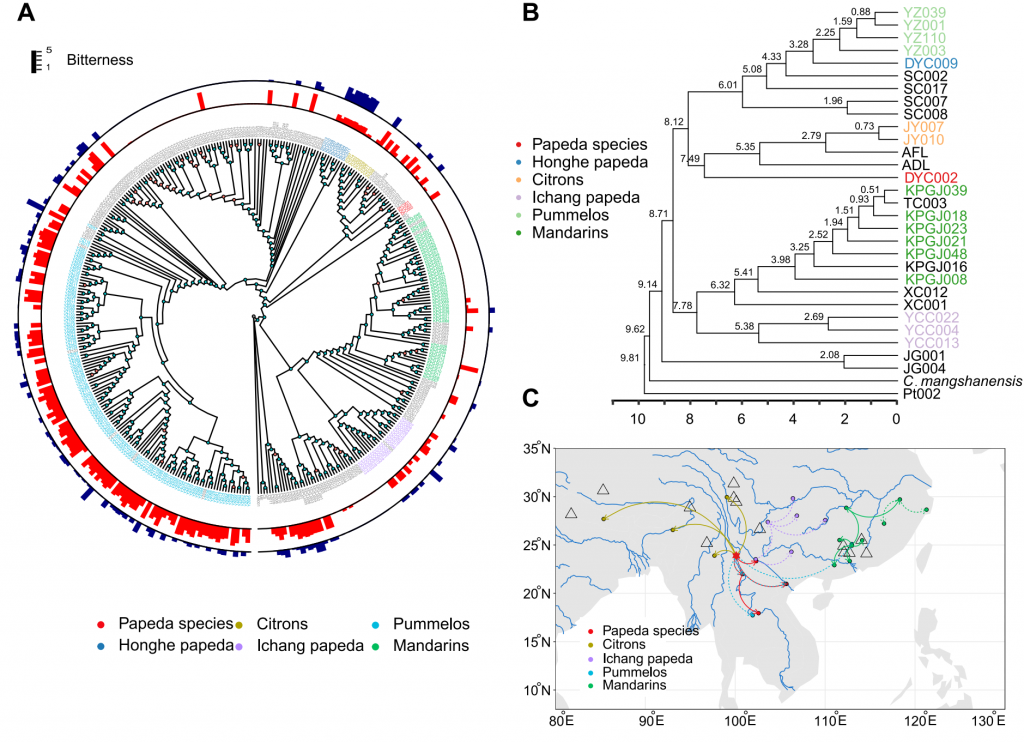
图3-群体进化分析
研究总结
高质量基因组的发表对了解柑橘发挥重要作用。然而,由于其复杂的遗传背景,许多柑橘物种的起源和进化仍不清楚。作者从头组装了DYC002的294mbp染色体水平的基因组,对两个单倍型基因组比较,发现了1.2%的基因组内变异,包括175 万个SNPs,149,471个插入和154,215个缺失。以该基因组为参考,对378份具有代表性的柑橘材料进行了重测序和系统发育分析,作者研究柑橘属可分为两个进化支,证实了柑橘核心种的主要起源中心是华南地区,特别是喜马拉雅-横断山脉。该研究为了解柑橘品种的起源和进化提供了新的视角,并可能为柑橘育种和改良提供有价值的基因组资源。
]]>

文章题目:T2T?genome,?pan-genome?analysis?and?heat?stress response?genes?in?Rhododendron?species
发表期刊:iMeta
影响因子:23.8
合作单位:贵州大学,华北理工大学
百迈客生物为此项研究提供基因组测序及部分分析服务。
研究亮点:
① 该研究首次报道了具有13条染色体的高质量端粒到端粒(T2T)的百合杜鹃基因组;
② 基于15个杜鹃属植物基因组,对杜鹃属植物进行了泛基因组分析;
③ 结合基因组测序和全转录组测序,鉴定了几个与热胁迫相关的关键基因和miRNA,为杜鹃属植物的比较基因组学和功能基因组学研究提供了丰富的资源。
研究背景
杜鹃花属于杜鹃花科,是木本植物中最大的属之一。全世界大约有1000种杜鹃花,中国是重要的分布中心。它们在喜马拉雅-横断山脉经历了进化辐射,横断山脉是世界生物多样性的热点。杜鹃花属植物因其观赏价值而在园艺中占有重要地位。全球气候变化导致温度升高,而热胁迫会影响植物的生长发育。然而,杜鹃花植物通常适应较冷的气候。利用多组学分析和分子生物学技术研究杜鹃花对高温胁迫的响应机制,对选育耐热品种、扩大杜鹃花栽培范围具有重要意义。
材料及方法
T2T基因组组装:Rhododendron liliiflorum
泛基因组分析:4个本次组装的基因组+11个已报到的杜鹃属基因组
全转录组:CK热处理、热处理3天(H3)和6天(H6)条件下进行了全转录组测序
两对具有代表性的miRNAs和相关靶基因进行功能验证。
研究结果
1.杜鹃属植物基因组测序、组装与评价
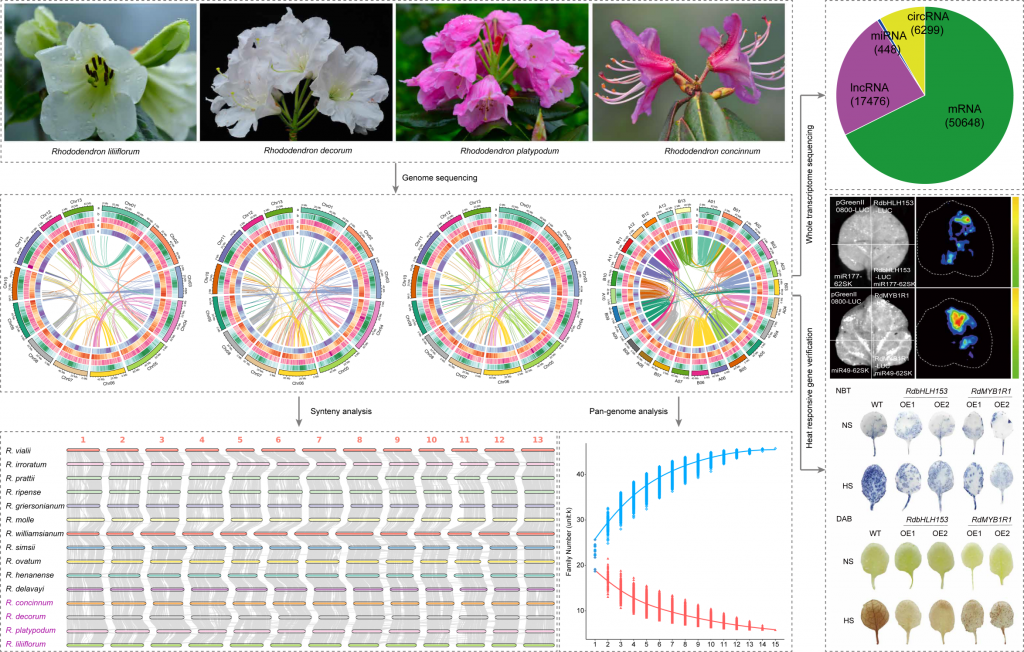
该研究通过PacBio HiFi、Oxford Nanopore Technology(ONT)、Illumina和Hi-C技术(图1A,表S1-6)对四种杜鹃花植物(Rhododendron liliiflorum、Rhododendron decorum、Rhododendron platypodum和Rhododendron concinnum)进行从头基因组测序。通过K-mer估算的R. liliiflorum、R. decorum、R. platypodum和R. concinnum的基因组大小分别为759.08 Mb、581.05 Mb、593.47 Mb和1356.22 Mb,并通过流式细胞术进一步验证(表S1,图1B)。
作者发现,R. concinnum的基因组几乎是其他三个物种的两倍大。因此,作者们利用流式细胞术进一步分析了染色体核型,首次发现R. concinnum为四倍体,核型为2n=4x=52,与其他三个二倍体物种(2n=2x=26)有明显差异(图1C,表S1)。
4个物种的基因组大小分别为793.25 Mb、649.87 Mb、652.27 Mb和1321.11 Mb(表S1)。经Hi-C检测,4个种的染色体锚定率均在97.90%以上(图1D,表S5)。作者获得了4个高质量的组装基因组,支架N50大于48.68 Mb。核心真核基因作图法(CEGMA)值从95.63%到99.56%,基准通用单拷贝同源序列(BUSCO)值从96.65%到97.34%,读取作图率超过99.40%(表S7)。
最重要的是,作者获得了一个高质量的R. liliiflorumT2T基因组,该基因组由13条染色体组成,检测到24个端粒和13个着丝粒(图S1A,表S8-11)。其中11条染色体在端粒与端粒之间没有间隙,另外2条染色体只有一个间隙。百合杜鹃花基因组的重叠群N50大于58.56MB,大于以往大多数杜鹃基因组的重叠群N50。采用BUSCO软件对基因组完整性进行评估(96.65%),基因组一致性质量值(QV)为43.71(表S1)。基因组LTR组装指数(LAI)值为21.15(图S1B),表明已达到最高质量水平(LAI≥20)。
重复序列占4个基因组的49.10%以上,以长末端重复序列(LTRs)最多(图1E,表S11)。在这四个基因组中,共预测到41406、41084、40556和83203个基因(表S12)。检测到超过97.15%的BUSCO基因,说明预测的完整性较高(表S13)。NR、eggNOG、GO、KEGG、TrEMBL、KOG、Swissprot和Pfam数据库对92.16%以上的基因进行了注释(表S14)。共检测到2355、4862、2852和9511个非编码RNA(表S15)。
2.15个杜鹃属植物泛基因组分析
杜鹃属植物以其多样的花朵展示而闻名,近年来,随着第一个R. delavayi基因组的公布,一些基因组被解码,引起了科学界的高度关注。报道了几种杜鹃属植物的基因组,如R. griersonianum、R. Henanense、R. Irroratum、R. kiyosumense、R. Ripense、R. Vialii、R. nivale和R. williamsianum。这些基因组为泛基因组研究奠定了基础。基于这四个高质量基因组以及11个先前发表的基因组,对杜鹃属植物进行了泛基因组分析(图1F,表S16)。选择T2T水平的R. liliiflorum基因组作为参考。该泛基因组通过添加394.57?Mb和14424个基因,扩展了T2T水平的R. liliiflorum基因组。15个物种的基因家族数量为45731个,包括5734个核心基因家族、37027个可有可无的基因家族和2970个私有基因家族(图1G、图S2A、表S17)。利用打乱图分析了15个物种间基因家族共享与唯一性的关系。最后,作者基于聚类分析构建了基因家族存在与否的分布图(图1H)。在2970个私有基因家族中,R.irroratum(1705)的物种特异性基因最多(表S17,图S2B)。功能富集分析表明,“倍半萜和三萜生物合成”和“亚油酸代谢”途径显著富集(图S3)。共鉴定出121185个核心基因,R. ovatum基因组的数量最多(9847)(图S2B)。功能富集分析表明,与花的颜色和香味相关的基因途径显著富集,如柠檬烯和蒎烯降解(图S4)。
3.15个杜鹃属植物基因组的变异分析
基于以T2T基因组为参考的泛基因组分析,作者对杜鹃花的单核苷酸多态性(SNPs)、插入和缺失(InDels)以及结构变异(SVs)等变异进行了全面鉴定(图1I-L,图S5)。四倍体R. concinnum具有最多的SNP(1876446)和InDels(447281)(图1I,表S18-19)。功能富集分析表明,含有SNPs和InDels的基因在“碳代谢”和“氨基酸生物合成”途径中显著富集。R. concinnum的SV数量最多,达到7694(表S20)。同时,作者进一步将SVs细分为重复(DUP)、易位(TRANS)和反转(INV),发现在大多数杜鹃属植物中,前者的数量超过后者(图S6-7)。SVs基因与SNPs或InDels基因相比表现出明显的模式,主要集中在RNA聚合酶和mRNA监控途径上。
4.15个杜鹃花基因组的LTR分析
该研究在15个杜鹃属物种的全基因组中鉴定了70759个LTR,其中R. griersonianum基因组的LTR数量最多(7323)(表S21)。作者发现,在过去的一百万年中,大多数杜鹃花物种只经历了一次插入事件的爆发,而R. delavayi、R. molle和R. williamsianum经历了两次插入事件的爆发。两个事件分别发生在1.53mya和2.94mya。作者对15个物种的LTR进行聚类,得到每个聚类中的共享LTR。结果表明,共有2622个LTR聚类,其中R. platypodum最多(531个)。R. liliiflorum中特异性LTRs数量最多(109个),而R. williamsianum中未发现物种特异性LTRs。聚类图显示,R.williamsianum与其他物种共享LTR的比例最高(图1M)。此外,LTR在染色体中部的分布密度大于两端(图1N)。
5.15个杜鹃属植物基因组的共线性分析
通过共线性分析,研究发现15个杜鹃基因组普遍表现出良好的共线性(图1O)。共线性区组数从336个(R. henanense?vs?R. delavayi)到692个(R. irroratum?vs?R. prattii)。此外,还发现了一些基因组转座现象,如R. ovatum7号染色体的末端区域与R. simsii和R. henanense。
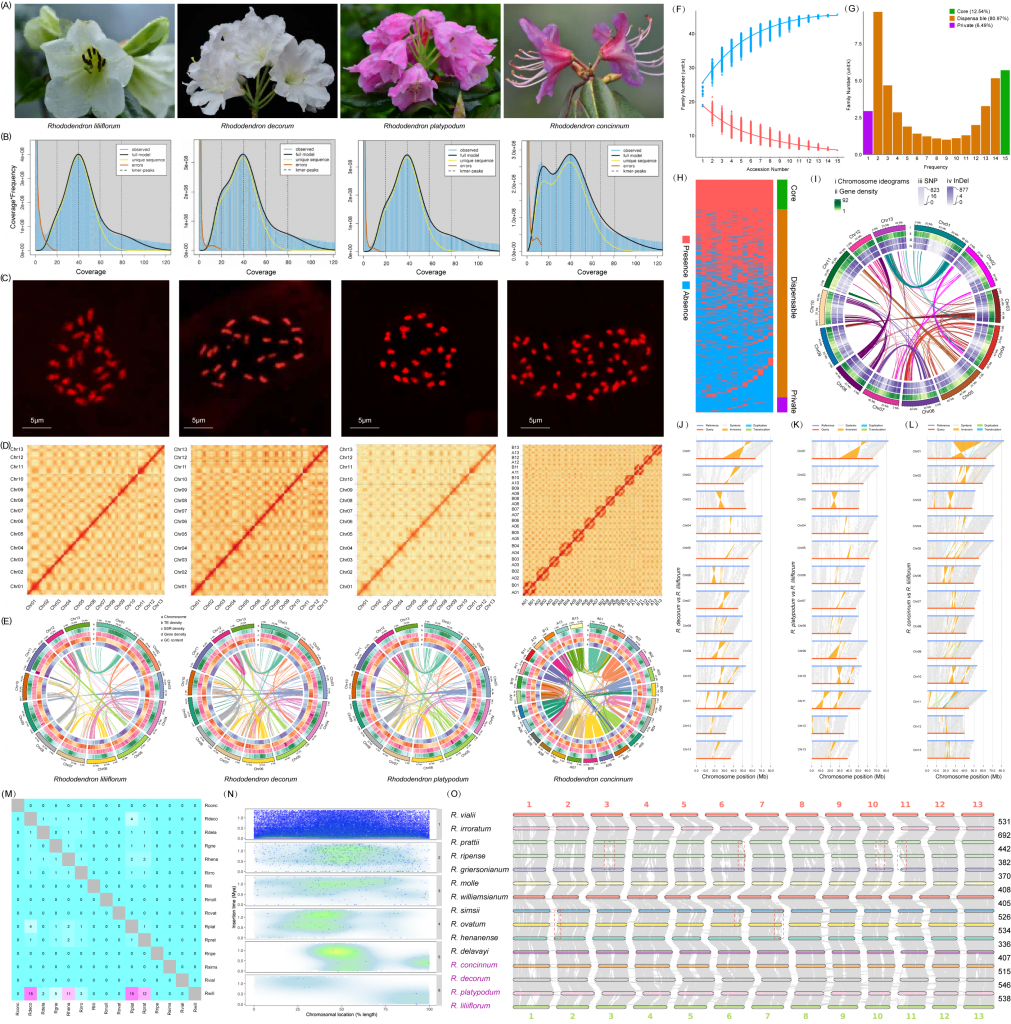
图 1. 4种杜鹃属及11种已发表杜鹃属植物的基因组分析 (A)四种杜鹃花的开花照片;(B)通过k-mer进行基因组调查。(C)流式细胞术检测染色体核型;(D)基因组组装的Hi-C接触图;(E)转座子、SSR、基因密度和GC含量在染色体上的分布;(F)核心(红色)和非核心(蓝色)基因家族数量趋势图;(G)核心集群、可有可无集群和私有集群的家族数量;(H)核心、可有可无和私有集群的存在和缺失分析;(I)百合杜鹃花基因组中基因密度、SNP和InDel变异的分布情况;(J-L)以T2T基因组为参照,研究了端粒红豆杉、鸭嘴兽和短柄红豆杉基因组的同源性和重排;(M)两个物种之间共享LTR的比例(Rconc:?R. concinnum; Rdeco:?R. decorum; Rdela:?R. delavayi; Rgrie:?R. griersonianum; Rhena:?R. henanense; Rirro:?R. irroratum; Rlili:?R. liliiflorum; Rmoll:?R. molle; Rovat:?R. ovatum; Rplat:?R. platypodum; Rprat:?R. prattii; Rripe:?R. ripense; Rsims:?R. simsii; Rvial:?R. vialii; Rwill:?R. williamsianum);(N)LTR在染色体上的分布。x轴代表染色体位置的百分比,y轴代表LTR的插入时间;(O)15种杜鹃属植物的基因组共线性。右边的数字表示共线块编号。
6.热反应基因的全转录组测序与检测
为了探索杜鹃花的耐热基因和调控机制,该研究在CK热处理、3天热处理(H3)和6天热处理(H6)条件下进行了全转录组测序(图2A,表S22)。共鉴定出50648个mRNAs、17476个lncRNAs、448个miRNAs和6299个circRNAs(图2B)。此外,在CK、H3和H6处理中,632个mRNAs、21个lncRNAs和6个miRNAs的表达和共享存在差异(图2C)。
7.候选基因的功能验证
该研究选择了两对具有代表性的miRNAs和相关靶基因进行功能验证。热处理后3h和6h,靶基因表达显著上调,小RNA表达显著下调。作者进一步研究了miR177对RdbHLH153(Rhdel02G0118700)表达和miR49对RdMYB1R1(Rhdel08G0208700)表达的影响。将萤火虫荧光素酶分别融合到RdbHLH153和RdMYB1R1的C端,并将miR49和miR177分别插入SK载体(图2D)。结果显示,RdbHLH153中的miR177和RdMYB1R1中的miR49的靶位点略有改变(图2E)。用RdbHLH153/RdMYB1R1与空SK载体(混合并渗透)或RdbHLH153与miR177(RdMYB1R1和miR49)的混合物对烟草单叶渗透区进行渗透。均显示荧光素酶信号的诱导,而R. delavayi中过表达的miR177和miR49可消除RdbHLH153/RdMYB1R1产生的信号(图2E-G)。
为了进一步研究RdbHLH153和RdMYB1R1在热胁迫中的作用,采用花浸法获得了过表达RdbHLH153和RdMYB1R1的转基因拟南芥株系(表S23)。36 h热处理后,转基因植株的生长明显优于WT(图2H)。经过热处理后,幼苗恢复正常状态5天,发现转基因植株转活,WT叶片全部变黄。说明RdbHLH153和RdMYB1R1在提高耐热性中起重要作用。DAB和NBT染色显示,与野生型植株相比,RdbHLH153/RdMYB1R1 OE株系中H2O2和O?2的含量显著降低(图2I)。
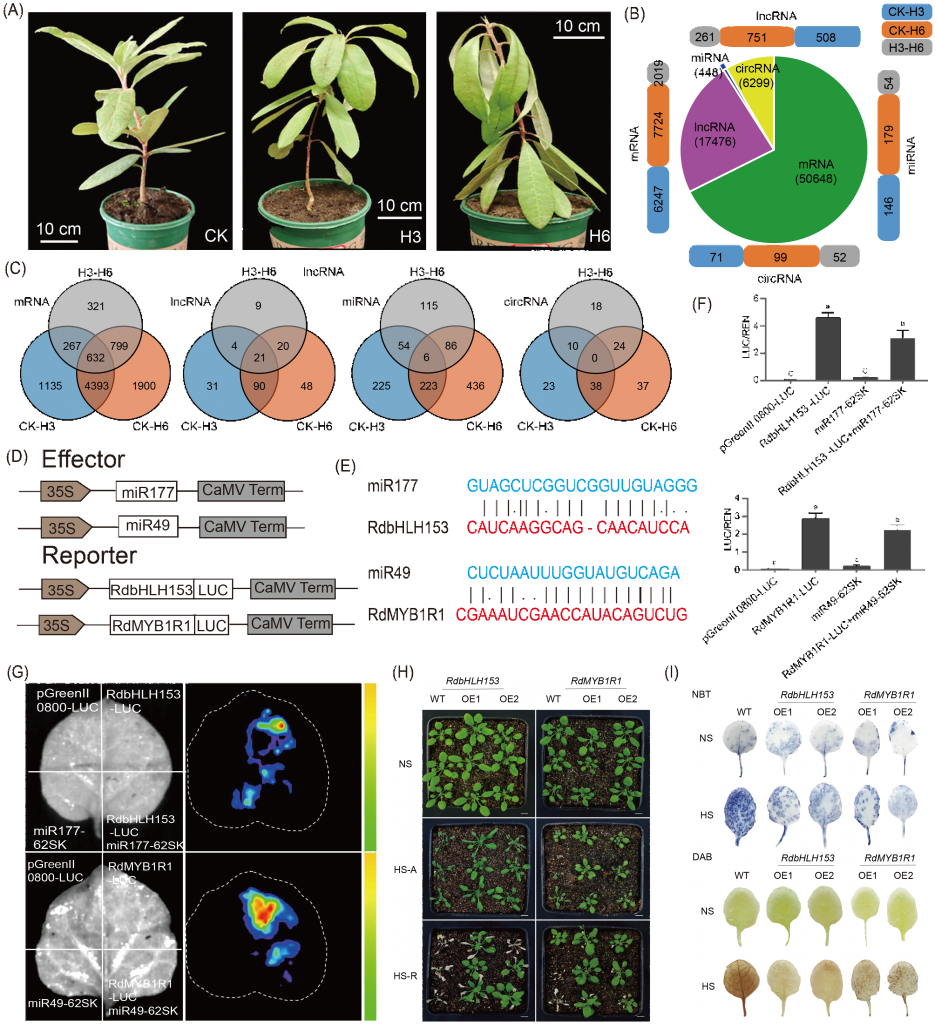
图2. miRNA和靶基因的全转录组分析及功能验证 (A)R. delavayi的对照(CK)和热处理(H3和H6);(B)mRNA、lncRNA、miRNA和circRNA的鉴定和差异表达分析;(C)三种比较中特异性和常见的差异表达RNA;(D)效应器和报告器结构图;(E)miR49和miR177靶点突变示意图;(F)荧光素酶测定统计。误差条表示三个重复的SEs(*,p?< 0.05)。(G)荧光素酶成像分析;(H)RdbHLH153和RdMYB1R1的过表达增强了耐热性。NS表示无热应激,HS-A表示36 h热应激,HS-R表示36 h热处理后在常温下恢复5天;(I)二氨基联苯胺(DAB)和硝基蓝四氮唑(NBT)染色法检测转基因株系和WT在无热胁迫(NS)和热胁迫(HS)下的H2O2和O?2。
内容来源于iMeta
]]>2025年3月,华中科技大学同济医学院附属同济医院器官移植研究所兰培祥教授、陈知水教授和肝脏外科程琪教授研究团队在Journal of Hepatology发表题为”Sour Neuronal Signalling Attenuates Macrophage Mediated Liver Injury”的研究论文。研究使用单细胞转录组测序技术等多种技术,深入阐述人鼠中减轻肝缺血再灌注损伤的脑-肝轴调控通路,发现酸味刺激竟然可以通过神经信号缓解肝脏损伤!这一发现不仅为肝脏疾病的治疗提供了新思路,还从现代科学的角度验证了中医“酸入肝”的理论。
文章标题:Sour Neuronal Signalling Attenuates Macrophage Mediated Liver Injury
期刊名称:Journal of Hepatology
影响因子:26.7
合作单位:华中科技大学同济医学院附属同济医院
百迈客生物为该研究提供了10X单细胞转录组测序技术服务。
研究背景
在中医理论中,酸味与肝脏有着密切的关系。中医经典《黄帝内经》中提到“酸入肝”,认为酸味食物能够滋养肝脏,调和气血,促进肝脏的生理功能。像柠檬、山楂、醋等酸味食物,常被用来调理肝气郁结、疏肝解郁。这次的研究,不仅让中医的古老智慧得到了科学验证,还为酸味在肝脏疾病治疗中的应用提供了新的依据。
肝损伤是多种肝病常见的病理生理基础,与炎症有关。肝缺血再灌注损伤是一种局部无菌炎症响应,主要由先天免疫细胞驱动,是肝切除术中早期器官功能障碍和衰竭的重要原因。传统认为肝缺血再灌注引起的炎症是由肝和死亡细胞释放的DAMP(损伤相关分子蛋白)被肝驻留库普夫细胞、单核细胞、单核-巨噬细胞等识别,释放趋化因子和促炎症因子,招募循环白细胞促使炎症发生。此外,近年来,神经免疫调控成为研究热点,科学家们发现,神经系统可以通过释放神经递质、神经肽等分子来调节免疫反应。然而,如何通过神经信号来治疗肝脏炎症,仍然是一个未解之谜。
材料及方法
研究方法:单细胞核转录组测序(n=3,肝及腹腔神经节),组织学染色,荧光染色,病毒示踪,免疫印记,免疫沉淀串联质谱,bulk RNA-seq,qRT-PCR,流式细胞术等。
研究材料:C57BL/6J小鼠缺血再灌注损伤模型,Fam19a2-/-Ccr2-/-小鼠,小鼠海马神经元细胞系HT122。
研究结果
1.酸刺激减轻肝缺血再灌注损伤
研究者首先构建酸刺激下肝脏缺血再灌注损伤(IRI)小鼠模型,发现酸刺激可以减少肝组织损伤以及血清标志物水平。但是,使用丁卡因局麻小鼠舌头或者灌胃柠檬酸不能减少肝损伤和血清标志物水平;NMDAR阻断剂1(阻断NMDAR介导的兴奋性突触传递)立体定位注射到腹后内侧核(VPN)后,酸刺激后IRI肝的血清标志物水平和肝损伤程度无明显变化,表明神经系统在酸刺激减轻IRI过程中起重要作用。此外,小鼠VPN注射示踪病毒的实验结果显示,肝脏以及CG(腹腔神经节)均检测到荧光,行腹腔神经节切除术能降低IRI肝的组织损伤和血清标志物水平,表明酸刺激减轻肝损伤过程通过脑-CG-肝轴。

图1-酸通过神经减轻小鼠肝脏缺血再灌注损伤
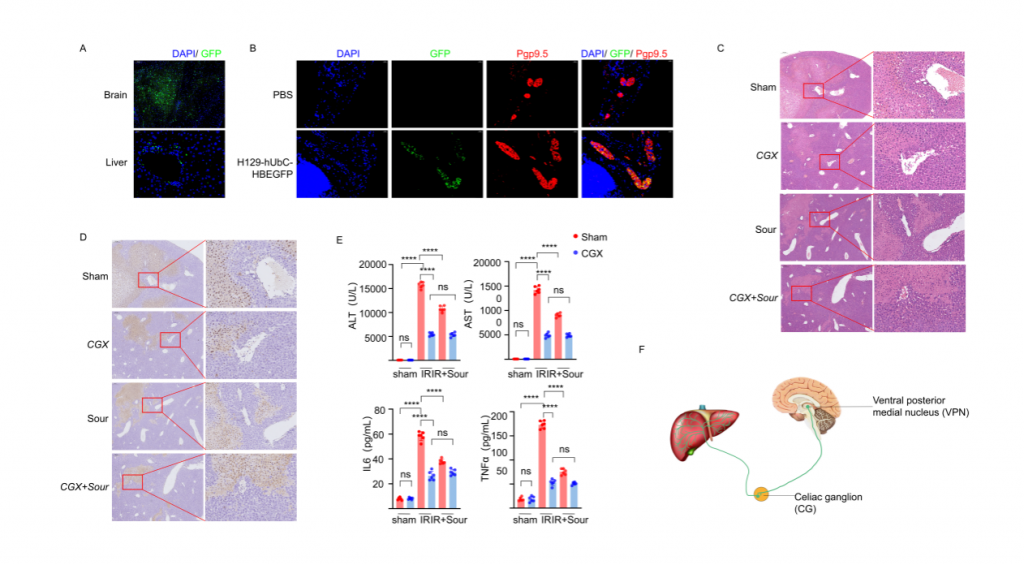
图2-脑和肝中分布的H129感染神经
2.酸刺激通过减少TAFA2产生降低肝IRI
对肝IRI小鼠、酸刺激后肝IRI小鼠及sham(假手术)小鼠的肝脏和CG进行单细胞核转录组测序,结果显示IRI引起肝细胞和神经元基因表达谱发生变化,IRI肝中免疫细胞数量增加,但酸刺激后IRI样本中免疫细胞数量减少。神经元较为特异性地表达TAFA2,IRI可引起肝神经元TAFA2表达水平增加,但酸刺激使得TAFA2表达水平降到与sham对照组相近水平。实验发现钾离子可引起小鼠海马神经元细胞系HT22显著高表达TAFA2,使用钾离子通道抑制剂可减轻肝损伤,支持酸刺激通过神经系统减轻肝损伤的假设。进一步的,使用慢病毒敲低神经元TAFA2表达水平或使用TAFA2敲基因鼠,发现IRI引起的肝组织损伤、巨噬细胞浸润以及血清标志物水平降低,表明TAFA2在肝IRI中有着重要作用。

图3-酸刺激减少小鼠IRI肝中神经细胞Fam19a2表达水平
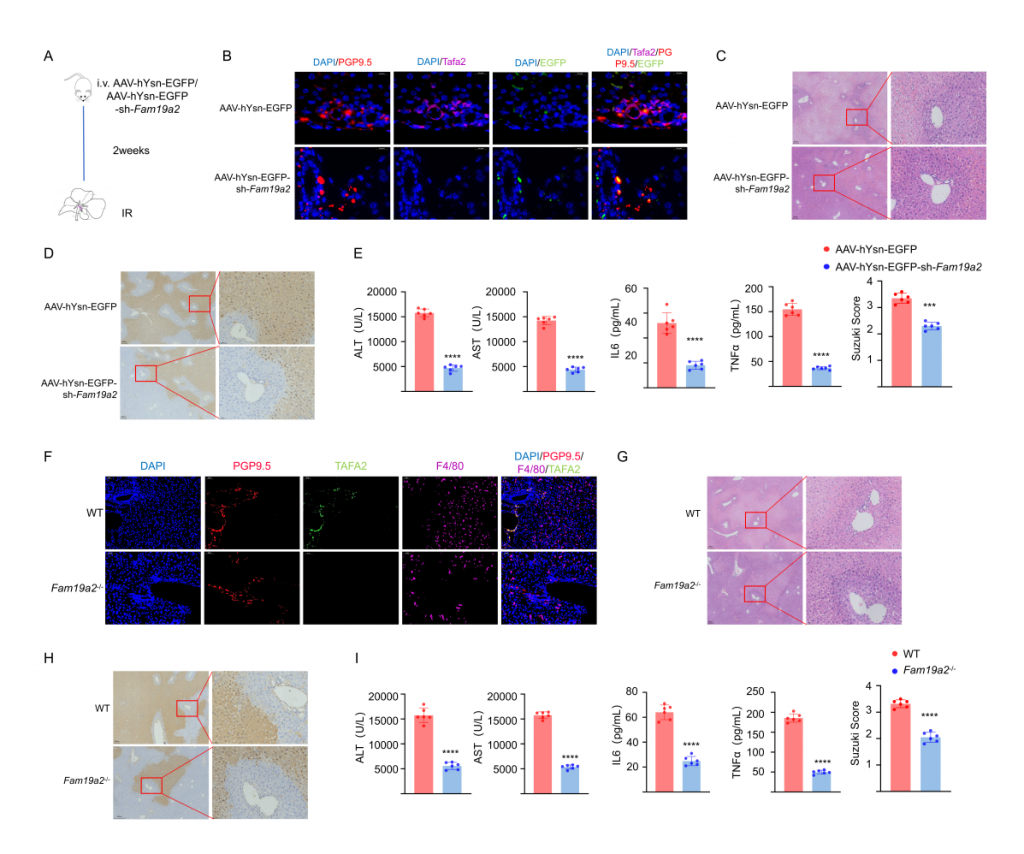
图4-Fam19a2敲除或敲低,使得小鼠肝脏缺血再灌注损伤降低
?3.IRI肝中TAFA2与巨噬细胞相互作用
体外实验发现TAFA2不引起肝细胞凋亡;snRNA-seq数据显示IRI肝中巨噬细胞比例增加且炎症相关基因表达水平增加,但在酸刺激组中降低;流式细胞术实验结果表明,TAFA2与巨噬细胞结合而不与T/B细胞结合,不论是否酸刺激T/B细胞比例无显著变化,IRI肝中CD11b+F4/80low?巨噬细胞增加而酸刺激可降低该巨噬细胞数量;TAFA2敲除或敲低抑制IRI肝中巨噬细胞的浸润,这些结果表明TAFA2促进巨噬细胞活化。体外实验结果表明,TAFA2可以激活BMDM(骨髓来源巨噬细胞),引起Il1α,Il1β,Il6和Tnfα的表达,这些结果表明TAFA2激活的巨噬细胞介导了肝IRI。
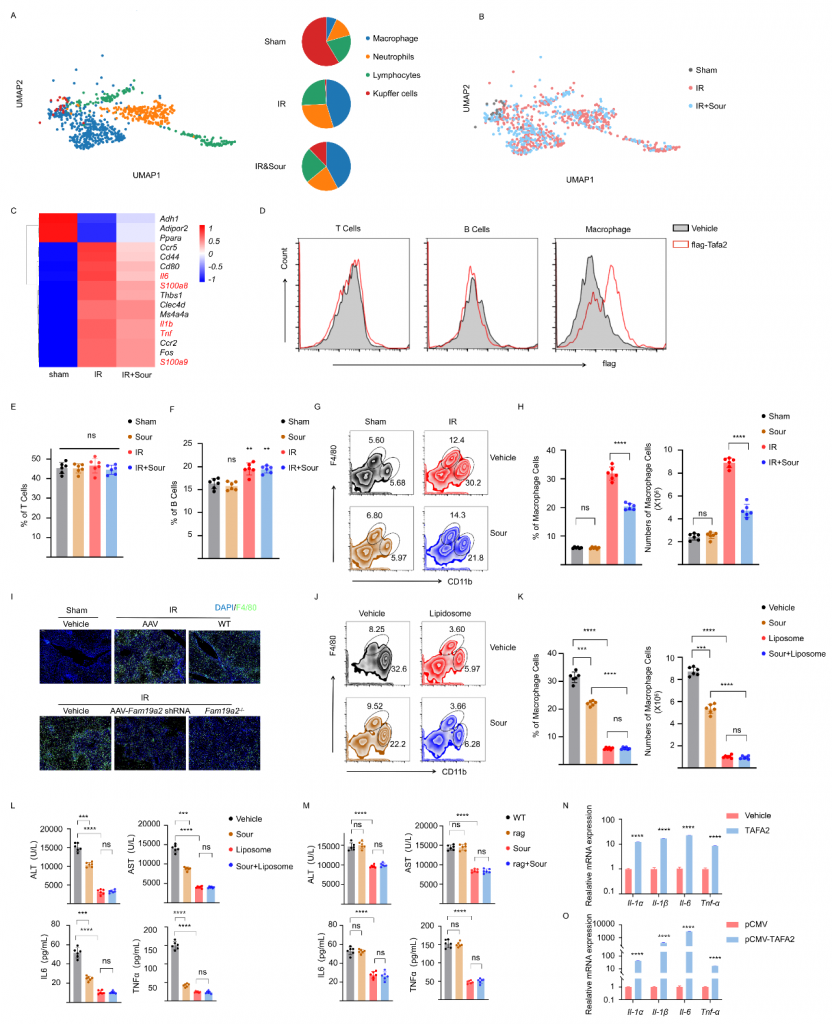
图5-TAFA2使得IRI中巨噬细胞比例增加,刺激炎性细胞因子的产生
4.TAFA2通过CCR2与巨噬细胞互作
体外实验表明巨噬细胞上的CCR2是TAFA2受体,CCR2敲除小鼠IRI肝的组织损伤以及巨噬细胞浸润降低,血清标志物水平降低。TAFA2或CCL2刺激后BMDM的bulk RNA-seq数据表现出几乎一致的转录组表达谱,粘附、代谢、Ras信号通路相关差异基因表达上调,代谢和核糖体通路相关基因表达下调,TAFA2诱导BMDM更高的表达Il1α,Il1β,Il6,Tnfα以及干扰素相关基因,促进巨噬细胞介导的炎症响应。进一步实验表明TAFA2促使巨噬细胞介导的炎症响应主要依赖CCR2,但巨噬细胞上也可能存在其他的TAFA2受体。
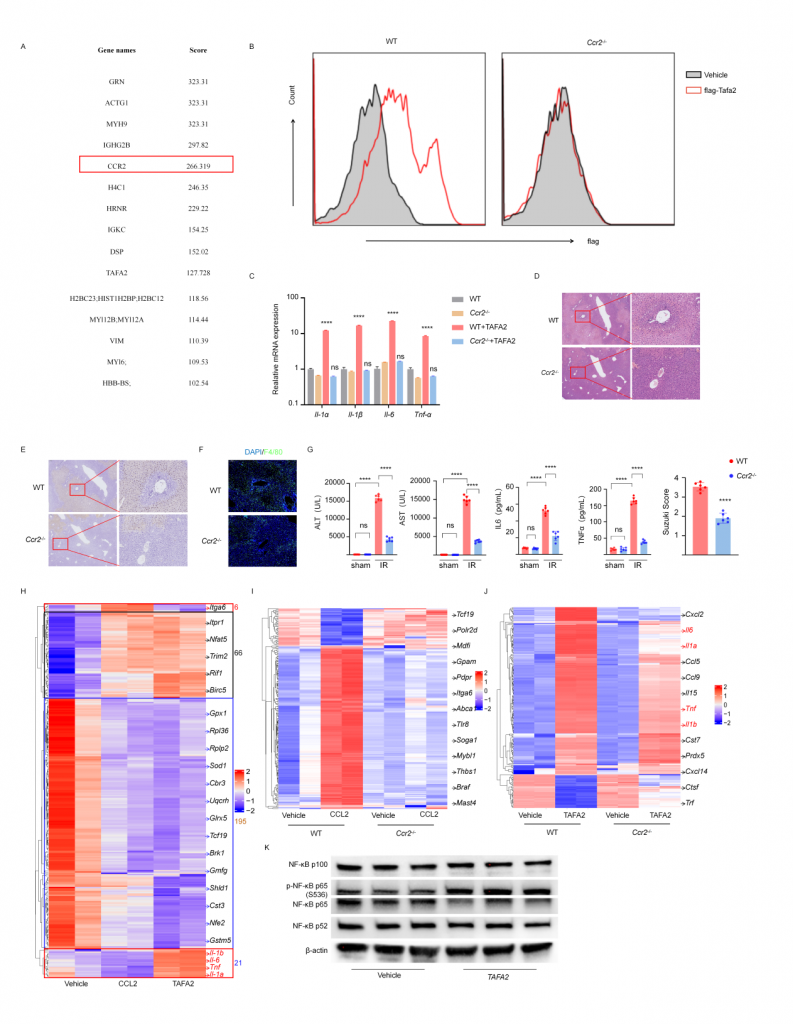
图6-TAFA2与巨噬细胞表面CCR2互作
5.酸刺激减轻人类肝切除术中肝IRI
为了确认酸刺激在人类肝IRI中的作用,研究者进行了开放、随机、空白对照临床试验(ChiCTR2400088096),包含多种良性/恶性肝肿瘤、肝外伤、脓肿、囊肿和包虫病,由于手术期间门静脉短暂阻断以减少肝切除过程中出血,导致肝出现缺血再灌注损伤。干预组33名患者,术前24h开始,每8h给与新鲜的25mM柠檬酸(持续5min),对照组33名患者不接受酸刺激,剔除6名术中肝缺血超过30min患者以及4名依从性差患者,肝切除术后第1/3/5天对患者肝功能进行评估,结果显示酸刺激组血清ALT和AST水平显著低于对照组,高ALT水平(>500 U/L)患者数量也显著更低,这些结果表明酸刺激可减轻人类肝切除术引起的肝IRI。
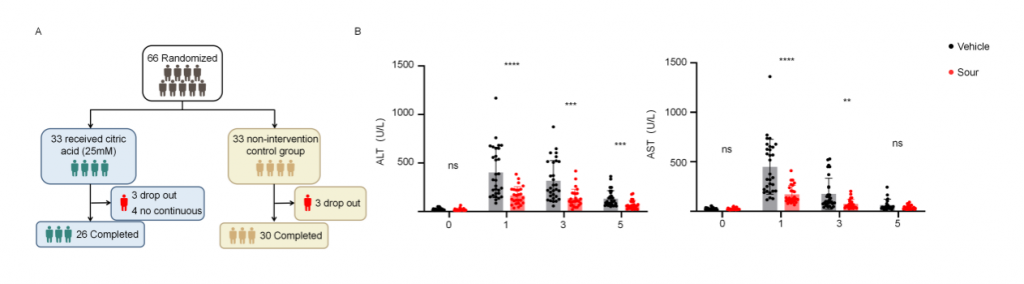
图7-酸刺激减轻人类肝切除术中肝IRI
研究总结
该研究首次揭示了脑-肝轴在肝脏IRI中的调控作用,阐明了酸味刺激通过神经信号通路缓解肝脏损伤的机制。研究不仅为肝脏IRI的治疗提供了新的思路,还为神经免疫调控在其他器官炎症中的应用奠定了基础。研究团队表示,未来将进一步探索神经刺激疗法在肝脏疾病中的应用,特别是通过调控脑-肝轴来缓解肝脏炎症和损伤。此外,研究团队还将深入研究TAFA2蛋白的作用机制,开发针对TAFA2-CCR2信号通路的靶向药物,为肝脏疾病的治疗提供更多选择。
]]>

研究背景
葡萄(Vitis)在全球范围种植广泛,即可鲜食又可加工成葡萄酒等,具有很高的经济价值,是农民致富、乡村振兴、人民美好生活中不可或缺的重要园艺作物。葡萄属于葡萄科葡萄属植物,该属包括两个亚属,麝香葡萄亚属(Muscadinia Planch)和真葡萄亚属(Euvitis Planch),共计70余个种;根据地理分布可将其分为三大类群,欧亚种群、北美种群和东亚种群。
葡萄作为最古老的驯化作物之一(约公元前11,000年),漫长的持续驯化和多年的育种改良导致现代葡萄品种的遗传多样性缩小和抗性丢失,使其易受病虫、逆境等各种不利条件的影响。近年北美葡萄泛基因组(Genome biology, 2023),欧洲葡萄泛基因组(Nature Genetics, 2024)的相继报道,野生葡萄以其丰富的遗传多样性和超强的抗性基因再次受到关注,但以大群体染色体级基因组组装为基础,涵盖主要品种,特别是包含东亚野生种葡萄的属级泛基因组一直未见报道。因此构建涵盖整个葡萄属的泛基因组将成为了解葡萄遗传多样性、开展功能基因组学研究、识别隐性遗传特性以及葡萄精准改良的关键资源。
材料方法及研究结果
该研究首先组装了酿酒葡萄(Vitis vinifera)霞多丽的完整单倍型基因组,并首次基于ChIP-seq数据鉴定了葡萄着丝粒序列,解析着丝粒的卫星重复序列结构特征,发现单倍型着丝粒之间的显著差异,表明其快速进化。其次,该研究通过对591个葡萄材料的群体基因组分析,选取了72个代表性葡萄材料(包括25个野生种和47个栽培种)进行染色体水平的单倍型基因组组装(图1),基因组验证表明这些单倍体基因组序列具有较高的质量和完成度。
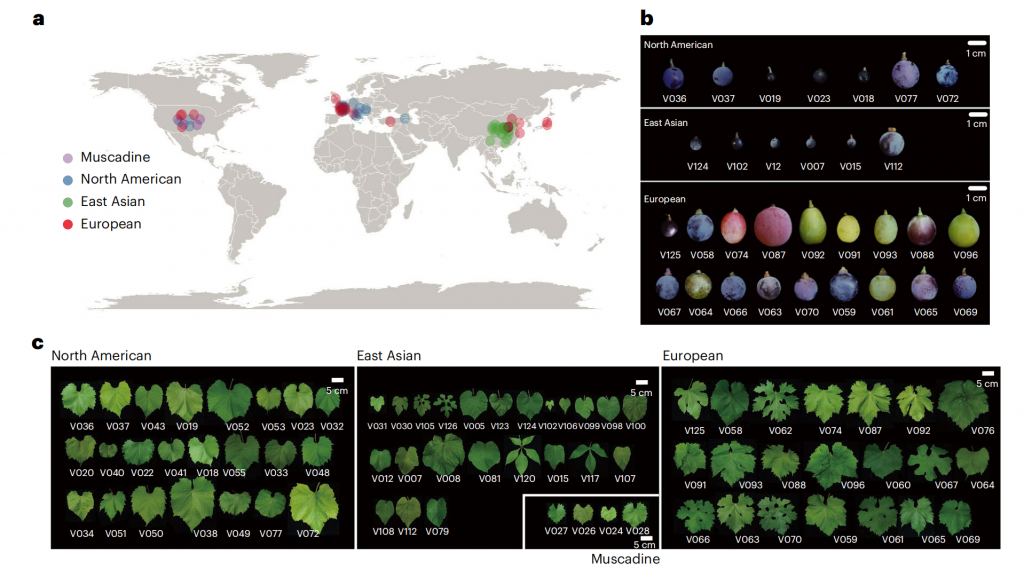
图1-葡萄样品全球地理分布及其果实和叶片形态
鉴于葡萄基因组因频繁杂交而具有的高度杂合性,单倍型基因组不仅能精确解析杂合区域序列,而且对分析葡萄的育种历史也至关重要。该研究构建了单倍型系统发育进化树,揭示了葡萄属植物复杂的育种历史和丰富的遗传多样性。结果显示,北美和欧洲品种存在较多内部杂交,而东亚品种的内部杂交较少,跨大洲杂交事件有限(图2)。特别是东亚葡萄极少被开发的遗传多样性,表明了其潜在的巨大育种价值。此次发布的东亚野生葡萄基因组为葡萄遗传育种研究提供了强有力的资源支持。
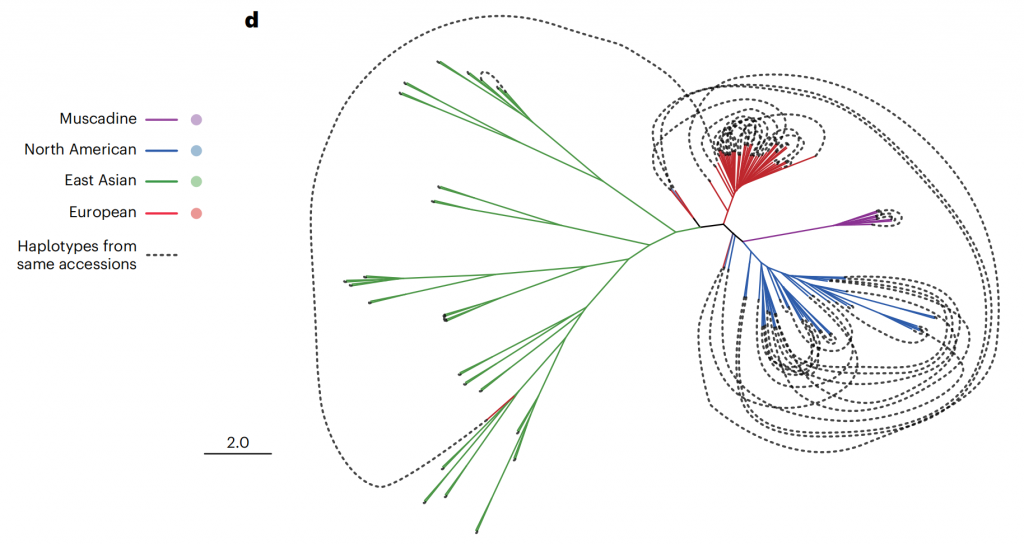
图2-144个单倍型基因组系统发育树
该研究还分析了72份葡萄材料的泛基因组家族,发现了超过6.4万个基因家族,包括不同数量的核心、可变和私有的基因家族。拟合曲线表明,该研究的泛基因家族数量趋向饱和,表明葡萄泛基因组接近闭合。研究还系统分析了葡萄属免疫受体蛋白基因家族NLR,结合三大种群的葡萄和圆叶葡萄抗霜霉病数据发现,TIR-NBARC-LRR家族的NLR基因在抗病(野生葡萄)和感病葡萄(栽培葡萄)中存在显著数量差异,因此有可能是葡萄抗霜霉病表型差异的重要因素之一。该超级泛基因组分析为研究葡萄属的遗传多样性、进化历史及功能基因挖掘提供了全面的基因组基础(图3)。

图3-葡萄属72份代表性材料超级泛基因组基因家族图谱
其次,该研究进一步绘制了目前比较完整的葡萄基因组遗传结构变异(SV) 图谱,助力挖掘与抗性及资源利用效率等重要性状相关的功能基因(图4)。该研究通过全基因组序列比对和变异检测,在67个Euvitis葡萄样本中鉴定出132,518个非冗余结构变异。功能富集分析表明,这些SV与葡萄叶片形态、病原识别及生物刺激感知相关。通过与已知分子标记的比较,该研究鉴定到霜霉病抗性分子标记Rpv3相关SV事件,并发现三大种群中该SV位点的不同单倍型与葡萄霜霉病抗性有显著关联性,证明该SV是一个关键抗病分子标记,突出了超级泛基因组图谱的价值。
图4-葡萄属72份代表性材料结构变异图谱
最后,该研究使用葡萄结构变异图谱和基于霞多丽完整基因组序列,构建了涵盖欧、亚、美三大种群的图形泛基因组。基于该图形泛基因组,该研究对113个葡萄样本的霜霉病抗性表型、气孔表型以及霜霉病侵染转录组数据进行了基因组变异的eQTL分析(图5),鉴定出63个SV-eQTL和1,808个SNP-eQTL与葡萄抗霜霉病显著相关。在63个与霜霉病抗性密切相关的SV的辅助下,该研究定位到一个氨基酸转运蛋白基因VvLHT8。进一步的分子功能实验发现VvLHT8可能通过负调控葡萄水杨酸合成和气孔免疫反应进而抑制葡萄抗病性,证实了高质量泛基因组辅助的多组学关联分析在作物重要农艺性状分子标记开发及功能基因挖掘中的高效性。该研究构建的葡萄属超级泛基因组不仅加深了对葡萄生物进化和育种改良的理解,也为精准改良葡萄抗病性和多样性提供了重要的科学基础。
图5-超级泛基因组图谱辅助SV-eQTL鉴定及VvLHT8基因功能验证
研究总结
该研究提供了比较全面的葡萄属基因组资源,有助于全面解析葡萄基因组的复杂性和多样性,从而高效发掘并利用葡萄特别是野生葡萄种中的优异基因。该研究结合葡萄属超级泛基因组、群体转录组学和表型组学,对葡萄属遗传多样性和重要农艺性状形成机制的深入探索,为未来培育超级葡萄提供了理论基础和新的思路(图6),标志着葡萄基因组研究迈进新的阶段,也必将加速推动我国葡萄种质创新和葡萄产业的高质量发展。
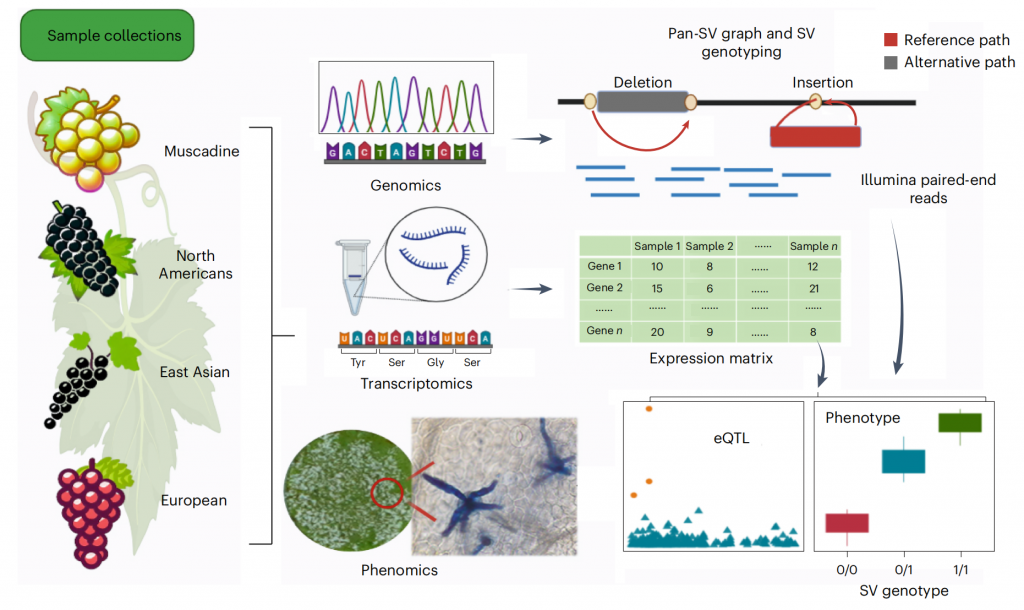
图6-葡萄属超级泛基因组构建和应用
以下小编列举三篇成功案例,解析群体在QTL定位中的应用。
当我们针对一群体,关注性状较多时,可参照案例一,整篇文章通过群体图谱构建,QTL定位后几乎没有验证工作,可以帮我们拿到一个群体QTL的基础数据。
案例一

发表期刊:Plant Physiology and Biochemistry
影响因子:6.1
合作单位:江苏省徐淮区徐州农业科学研究所农业农村部甘薯生物学与遗传改良重点实验室
实验方法:Xin24×Yushu10杂交中选择212个F1材料: 特异性位点扩增片段测序(SLAF-seq);遗传图谱构建;数量性状位点(QTL)定位;GWAS关联(F1群体)
表型检测:多年多表型收集
百迈客生物为该研究提供了群体测序及部分数据分析服务。
甘薯作为一个全球重要的作物,其含有丰富的营养成分以及对不同环境的适应能力。然而,由于其自交不亲和,高杂合度等特性,使其遗传特征的研究相对较少。作者从Xin24×Yushu10杂交中选择212个F1材料,SLAF-seq测序,获得亲本26.73×,子代52.25×的测序数据,依据SNP及百迈客生物自主研发的HighMap构图软件,生成一个长度为2441.56 cM、平均图距为0.51 cM的遗传图谱。
基于连锁图谱,鉴定出26个QTL,解释了6.3-10%的表型变异,包括6个最长藤蔓长度 QTL、6个单株产量 QTL、10个干物质含量QTL、1个淀粉含量 QTL、一个可溶性糖含量QTL和2个类胡萝卜素含量QTL。该研究结果对甘薯的标记辅助育种和基因克隆具有重要意义。
图1-表型检测
图2-遗传图谱构建
图3-QTL定位
前文是对多个性状的连锁分析,当我们关注单个性状时,BSA无疑是高性价比的初定位选择,当然,这就意味着我们得做到基因的精细定位与克隆,除去传统图位克隆的方式,转录组,蛋白组,自然群体GWAS,基因组都可助力基因克隆,如果想发高水平的文章,基因的功能探索也是必不可少的。
成功案例二

发表期刊:Plant Biotechnology Journal
影响因子:10.1
发表单位:河南农业大学
实验方法:荚果大小/重量差异显著2份Virginia-type花生材料( ND _ L和ND _ S)杂交,产生遗传群体;F2:3群体BSA-seq(20+20混池);F6:7 和F6:8群体精细定位;基因克隆;系统进化分析;亚细胞定位;免疫荧光;酵母双杂交;pull-down;CO-IP;番茄拟南芥转化实验等。
百迈客生物为该研究提供了群体测序及部分数据分析服务。
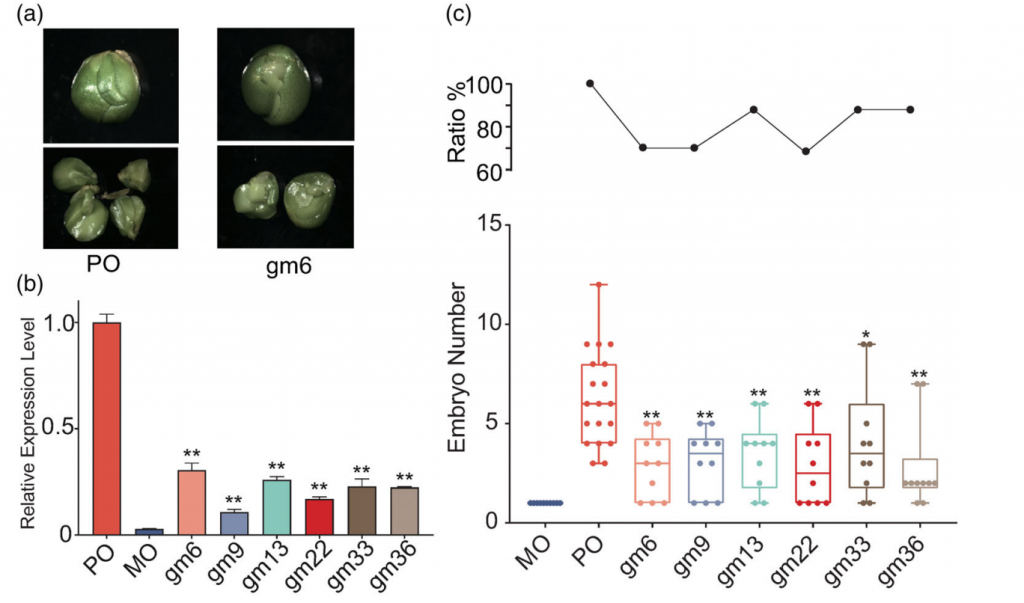
花生荚果大小是决定花生产量的关键农艺性状,为了鉴定控制花生荚果大小的基因,该研究对188份核心种质进行鉴定,并选取荚果大小/重量差异显著的2份花生材料构建F2群体,BSA-Seq获得了288.58 Gb的原始数据。利用285914个高质量SNPs 和70 759个 InDel,将控制荚果大小的基因定位在07染色体1.17 Mb的区间内。作者从F6:7和F6:8群体中开发了15个多态性标记并对个体进行基因分型,精细定位QTL到KASP 9 和In Del15之间20.4 kb的区间内。该区间仅包含1个预测的非同义突变基因和InDels,将该基因命名为PSW1。
PSW1编码一个LRR – RLK蛋白激酶,等位基因PSW1HapII赋予了PSW1更高的表达水平和对其辅助受体AhBAK1更强的亲和力,以上调PSW1 – based途径,调节花生荚果大小。此外,PSW1HapII的过表达增加了多种植物的种子/果实大小。
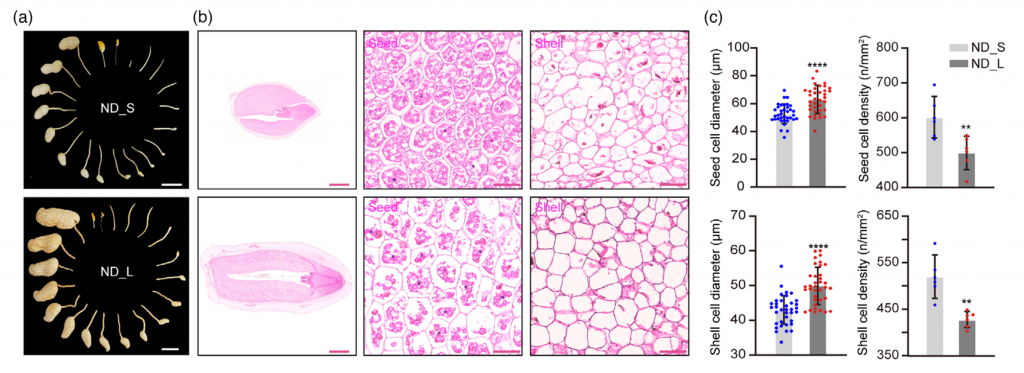
图4-表型检测
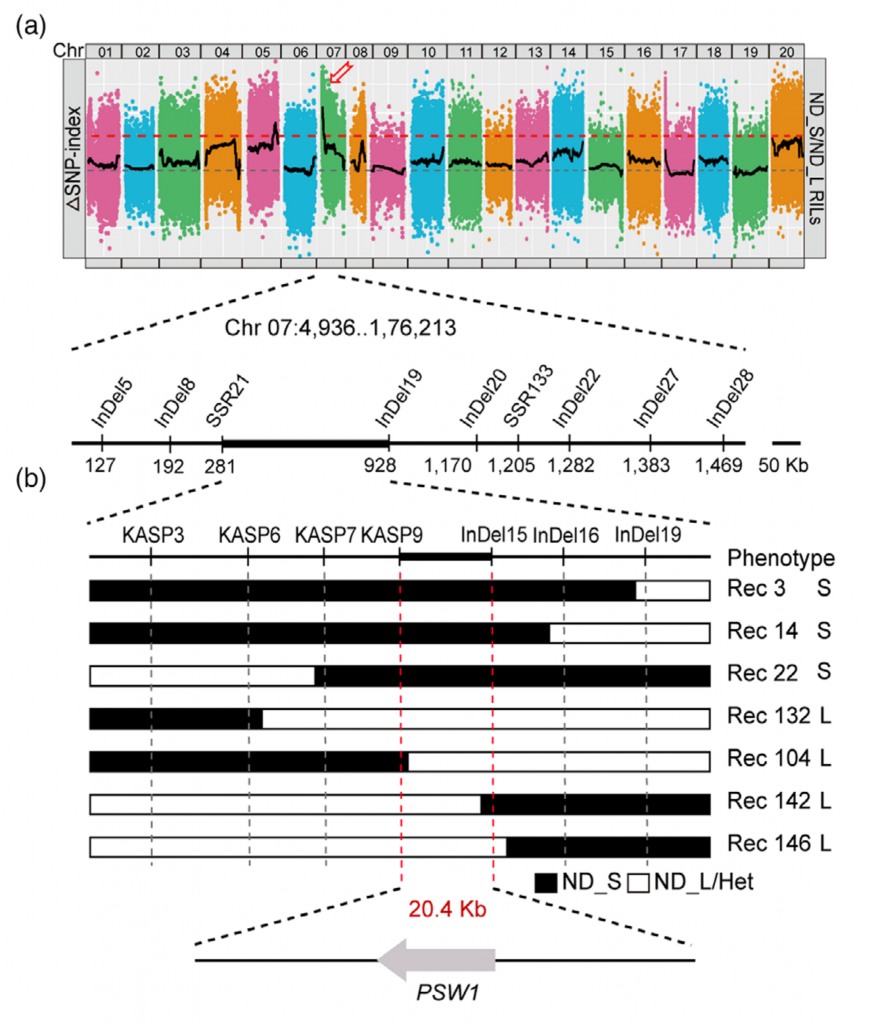
图5-BSA分析
当然,如果想让我们的文章影响因子再上一台阶,兼顾群体的“广度”和“深度”,是更好的选择。
成功案例三

发表期刊:Nature?Genetics
影响因子:30.8
发表单位:浙江省农业科学院等
实验方法:菜用豇豆G98,粮用豇豆G323 基因组Denovo;重测序GWAS:344份全世界收集的豇豆核心种质,其中包括342份栽培豇豆(87份粮用豇豆、244份菜用豇豆和11份未知用途豇豆)和2份野生豇豆;Illumina测序,10x深度;基因单倍型验证:菜用豇豆地方品种 ‘ZN016’ 和菜用豇豆育成品种‘Zhijiang282构建的RIL群体(183 lines)G98和G323构建的F2群体(165 individuals)
百迈客生物为该研究提供了群体测序、基因组测序及部分数据分析服务。
豇豆起源于非洲,在世界范围内作为粮食、蔬菜或牲畜饲料种植。该研究结合PacBio、Hi-C和二代测序,组装了粮用豇豆和菜用豇豆的染色体水平基因组。对包括地方品种、野生品种和育成品种的344个材料进行二代测序,以阐明豇豆基因组的系统进化。
为了研究自然或人工选择对豇豆分化的影响,作者通过选择清除分析比较了三个豇豆亚群之间的基因组选择特征,鉴定出239个与豇豆驯化和改良相关的基因。此外,通过GWAS,挖掘到裂荚性、荚长、单荚粒数、千粒重、可溶性糖、总淀粉和粗蛋白质含量相关基因,并在遗传群体中验证。同时揭示了两个亚种之间基因组结构变异(SVs)的全图谱,为豇豆在全基因组选择下的驯化与改良提供了见解。产量性状和品质性状的差异基因组选择将有助于建立粮用豇豆和菜用豇豆双向改良的遗传资源。

图6-群体选择与GWAS分析
今日分享结束,期待下期精彩内容~~~
]]>
近日,中国科学家发现一株神奇菌株Sinomonas gamaensis NEAU-HV1,它通过重塑植物关键蛋白互作网络,打破生长抑制枷锁,让作物产量飙升!成果登上国际顶刊!

中文标题:《Sinnomaras gamaensis NEAU-HV1通过重塑IAA14-ARF7/19互作促进植物生长》
英文标题:Sinomonas gamaensis NEAU-HV1 remodels the IAA14-ARF7/19 interaction to promote plant growth
发表期刊:New Phytologist
影响因子:10.2
合作单位:南京农业大学、东北农业大学
百迈客生物为该研究提供了高通量绝对定量测序及分析等相关工作。
破局:植物生长的“分子开关”被重新编程
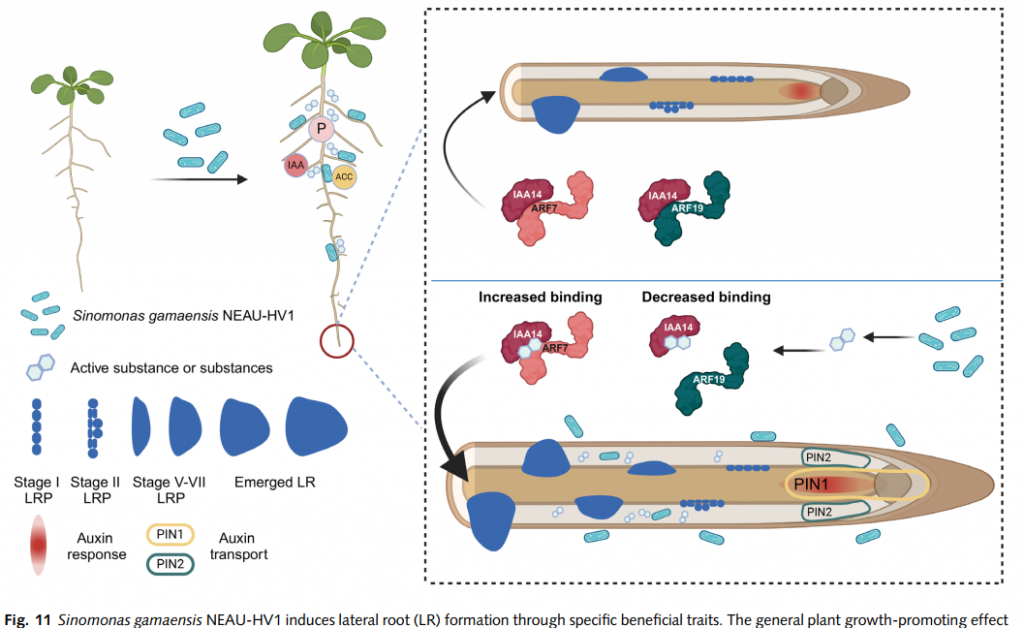
植物生长素信号通路中,IAA14蛋白是关键的“刹车控制器”——它与生长素响应因子ARF7/19结合时,会抑制下游促生长基因表达。传统促生菌多通过分泌激素“强推”生长,但NEAU-HV1菌株另辟蹊径:它直接改写IAA14与ARF7/19的互作模式,让“刹车”松动,植物自主释放生长潜能!
核心发现:NEAU-HV1对生长素信号的影响可能通过重塑SOLITARY-ROOT(SLR)/IAA14与ARF7/19的互作实现,且该过程不依赖生长素受体TIR1/AFB2,为植物-微生物互作机制提供了新见解。
文章核心内容
- 材料与方法
① 菌株与培养条件
NEAU-HV1 分离自棉田土壤,使用TSB培养基(28°C,250 rpm)培养。
对照菌株:解淀粉芽孢杆菌FZB42和伯克霍尔德菌CC-A174。
② 植物材料与处理
拟南芥(Col-0野生型及突变体)、生菜、小麦、玉米、花生等。
细菌悬液(10?–10? CFU/ml)处理种子或幼苗,评估生长表型。
③ 促生长特性分析
溶磷能力(NBRIP培养基)、ACC脱氨酶活性(DF培养基)、IAA产量(HPLC检测)。
④ 根际定殖能力
高通量测序结合内标法定量NEAU-HV1在根际和根内的动态丰度。
⑤ 分子机制解析
转录组分析、酵母双杂交(Y2H)、双分子荧光互补(BiFC)、微量热泳动(MST)等技术验证IAA14-ARF7/19互作。
- 研究结果
① NEAU-HV1显著促进作物生长
生菜、小麦、玉米、花生的生物量(鲜重、干重)和根系长度显著增加。
田间试验中,NEAU-HV1处理使花生株高增加56.4%,蛋白质含量提升16.5%。
② 多效性促生长特性
溶磷指数(PSI=4.1)、IAA产量(22.14 μg/ml)、ACC脱氨酶活性均优于对照菌株。
③ 根际与内生定殖能力
接种20天后,根际和根内菌量分别达4.2×103和7.6×103 copies/g鲜重。
④ 代谢物通过生长素信号诱导侧根形成
NEAU-HV1代谢物促进侧根原基(LRP)从阶段I向VII的发育,且不抑制主根伸长。
该过程依赖 IAA14-ARF7/19 信号模块,但与TIR1/AFB2受体无关。
- 研究讨论
传统研究多停留在微生物的“有无”层面,而本研究通过高通量微生物绝对定量技术,将含量多少转化为精确的拷贝数数据,如同为细胞安装“纳米级传感器”。本研究首次揭示 S. gamaensis NEAU-HV1 通过分泌代谢物重塑IAA14与ARF7/19的互作,独立于经典生长素受体激活侧根发育。其多效性促生长特性(溶磷、产IAA、根际定殖)及对脂肪酸组成的调控(增加短链饱和脂肪酸)展现了广阔的农业应用潜力。未来需进一步解析其活性代谢物的化学结构,以深化对植物-微生物互作机制的理解。
技术亮点
- 微生物高通量绝对定量使用:说明菌的绝对拷贝数与植物生物量成正比。
- 动态范围提升10倍:可检测到低至1 fmol/μg的蛋白互作变化,灵敏度远超传统方法。
- 时间分辨率突破:连续监测处理0-72小时内IAA14-ARF7/19复合物的动态解离曲线,揭示菌株作用的“黄金窗口期”。
应用前景:从实验室到田间
- 增产革命:在玉米、水稻试验中,NEAU-HV1处理组生物量平均增加35%,且无需额外施肥。
- 抗逆潜力:初步数据显示,该菌株可缓解盐胁迫下植物的生长抑制,未来或成“抗逆基因开关”。
- 绿色农业:取代化学激素,减少环境污染,契合碳中和目标。
结语
从分子开关的精准调控到绝对定量技术的革新,这项研究不仅解锁了植物生长的“隐藏技能”,更展现了合成生物学在农业领域的无限可能。未来,我们或许只需一株工程菌,就能让万亩良田“自主升级”!
]]>
- 发表期刊:Cancer Cell
- 影响因子:48.8
- 发表日期:2025-2-6
- 发表单位:中国医学科学院肿瘤医院
- 课题切入点:本文研究了三阴性乳腺癌(TNBC)中不同治疗方案对肿瘤免疫微环境(TME)的影响,特别是探讨了化疗与程序性死亡配体1(PD-L1)阻断联合疗法的细胞机制。
- 研究?材料?:研究从44名TNBC患者中获取了78份肿瘤活检样本,包括接受nab-紫杉醇(Nab-PTX)联合阿替利珠单抗(ATZ)、Nab-PTX单药、紫杉醇(PTX)联合ATZ以及PTX单药治疗的患者。
- 研究方法?:采用单细胞RNA测序(scRNA-seq)和T细胞受体测序(TCR-seq)技术,对TNBC中的免疫细胞浸润进行了详细分析。此外,还利用小鼠4T1乳腺癌模型进行了体内验证实验,包括RNA测序和流式细胞术分析。?·?研究结论?:研究发现,不同治疗方案下,TNBC中的免疫细胞组成发生显著变化。Nab-PTX联合ATZ治疗显著减少了耗竭性CD8+T细胞(Tex)的比例,同时增加了具有干细胞样特征的中央记忆T细胞(Tcm)和效应记忆T细胞(Tem)的比例。B细胞亚群,特别是滤泡B细胞(Bfoc),在Nab-PTX联合ATZ治疗的响应者中显著富集,且B细胞水平与有利反应相关。此外,研究还揭示了不同DC亚群之间的转化关系,以及它们与T细胞反应之间的相互作用。肥大细胞在Nab-PTX相关治疗中显示出增加的趋势,且其浸润水平与有利反应相关。体内实验进一步证实了肥大细胞激活可以增强抗肿瘤免疫反应,从而提高PD-L1阻断疗法的有效性。
这些发现不仅增进了我们对TNBC中免疫细胞动态及其与治疗反应之间关系的理解,还为开发新的化疗免疫联合疗法提供了潜在的治疗靶点。

- 发表期刊:Annals of Oncology
- 影响因子:56.7
- 发表日期:2025-2-4
- 发表单位:英国伦敦癌症研究所和英国伦敦皇家马斯登医院
- 课题切入点:该研究探讨了基于全基因组测序(WGS)的超灵敏循环肿瘤DNA(ctDNA)检测技术在早期乳腺癌分子残留病灶(MRD)监测和复发预测中的应用。· 研究样本:研究团队分析了78例早期乳腺癌患者(包括23例三阴性乳腺癌、35例HER2阳性、18例HR阳性及2例未知亚型)的617份血浆样本,覆盖诊断前、新辅助化疗期间、术后及长期随访(中位随访76个月)多个时间点。患者血浆样本来自英国多家医疗中心,包括诊断前、新辅助化疗周期、术后及定期随访样本。
- 研究方法:对肿瘤组织进行全基因组测序(中位深度38×),筛选高可信度体细胞变异构建个性化检测panel。血浆游离DNA(cfDNA)经高通量测序后,通过分子共识算法抑制背景噪声,计算ctDNA水平。所有样本通过NeXT Personal MRD平台进行检测,该平台基于肿瘤组织的全基因组测序数据,为每位患者个性化设计检测panel,追踪中位数1451个体细胞变异,检测灵敏度可达百万分之一(1 PPM)。
- 数据分析:采用Kaplan-Meier生存分析和Cox比例风险模型评估ctDNA检测与临床结局(复发无生存期RFS、癌症特异性生存期CSS)的关联,并通过时间依赖性模型动态评估MRD状态对预后的影响。
- 研究结果:1. 诊断阶段:98%(49/50)的患者在治疗前检测到ctDNA,涵盖所有亚型(HER2+和TNBC均为100%,HR+为88%)。诊断时ctDNA水平升高与较差的RFS(HR=1.82)和CSS(HR=2.19)显著相关。2. 术后监测:所有复发患者(11/11)在临床复发前均检测到ctDNA(中位提前15个月),未检测到ctDNA的患者(64/64)均未复发。术后ctDNA阳性与RFS和CSS显著恶化相关(均P<0.0001)。3. 灵敏度优势:39%的ctDNA阳性样本处于超低水平(<100 PPM)。与全外显子测序(WES)和数字PCR(dPCR)相比,WGS方法在匹配样本中检测率更高(WGS 100% vs. WES 84% vs. dPCR 76%)。4. 动态预后:术后6周或6个月未检测到ctDNA的患者预后显著改善。此外,术后早期ctDNA清除(如辅助治疗后)可能提示疾病控制良好。
- 研究结论:WGS驱动的超灵敏ctDNA检测技术显著提升了早期乳腺癌MRD监测的敏感性和特异性,可提前预测复发并指导临床决策。其高阴性预测值(NPV 100%)支持在低风险患者中探索治疗降阶梯策略,而阳性结果则为早期干预提供了依据。未来需扩大样本量并开展前瞻性研究以验证其临床实用性。
Ps:关注医学领域肿瘤研究请联系当地业务经理获取原文~
]]>
猪不仅是重要的经济家畜,还在科研中扮演重要角色。猪器官与人类器官高度相似,被广泛用于临床前研究。
2020年,马斯克展示了植入脑机芯片的猪,展示了脑电波信号的变化;2021年以来,全球已完成猪器官移植到脑死亡患者的实验;2025年,空军军医大学西京医院又一次成功实施了猪肝脏异种移植到人脑死亡患者体内,与之前不一样的是,这次是切除人类肝脏后只保留猪肝脏,探讨猪肝能否完全替代人肝。
从时空实验应用条件看,猪的器官组织特征与人类接近,实验开发难度较低。猪是二倍体生物,基因组质量良好,有基因表达调控数据库和单细胞数据,便于跨物种比较研究。综上,时空技术的应用可提升研究精度,为后续研究提供精准参考。
生殖方向
1.猪早期卵子发生的时空图谱

英文标题:Spatiotemporal dynamics of early oogenesis in pigs
发表期刊:Genome Biology
影响因子:10.1
发布时间:2025-01
DOI:10.1186/s13059-024-03464-8
实验设计时空部分:
单细胞转录组,猪E45、E55、E65、E75胚胎卵巢(n=2)。
空间转录组,猪E45、E55、E65、E75胚胎卵巢,10x Visium;E65胚胎卵巢,BMKMANU S1000。
百迈客生物为该研究提供了百创S1000空间转录组技术服务。
研究内容总结:
① 该研究结合单细胞RNA测序(scRNA-seq)和空间转录组学(ST)探索在猪卵子发生早期卵巢微环境的空间组织,构建时空基因表达谱。将卵子发生不同阶段的生殖细胞簇投射到空间图谱中,揭示了发育中的猪卵巢中生殖细胞的“皮质-髓质(C-M)”分布。猪和人之间的跨物种分析揭示了在卵子发生过程中生殖细胞的保守的C-M分布模式,提示猪可以作为人类早期卵子发生过程的理想研究模型。
② 利用ST数据进行RNA速度分析,确定了猪卵巢皮质和髓质区颗粒细胞系的分子特征和空间动力学。通过空间共定位分析和细胞间通讯分析,揭示了皮质和髓质区域生殖细胞和体细胞之间独特的细胞-细胞通讯模式。
③ 值得注意的是,卵巢组织的体外培养实验结果证实细胞间NOTCH信号传导和细胞外基质(ECM)蛋白在启动减数分裂和卵子形成程序中起关键作用,表明卵巢微环境对于生殖细胞的命运调控起着重要作用。

图1-基于Cell2location,使用scRNA-seq数据对ST数据进行解卷积
2.时空技术解析猪滋养层类器官与母胎界面细胞多样性

英文标题:Defining Cellular Diversity at the Swine Maternal-Fetal Interface Using Spatial Transcriptomics and Organoids
发表期刊:bioRxiv
发布时间:2024-10
DOI:10.1101/2024.10.21.619461
实验设计时空部分:单细胞转录组,滋养层细胞系类器官(n=3)。空间转录组:G65脐带残端附近1cm*1cm完整胎盘(包括母体和子代组织,n=4)。
研究内容总结:
① 研究者使用足月猪胎盘构建的sTO(猪滋养层类器官)可以扩增、冻存并成功复苏,高表达滋养层标志基因KRT18、ELF3以及GATA3,与猪胎盘表达标志更相似。此外,在人工基底膜中培养立刻形成悬浮培养可逆的局部顶面,通过和体内较为一致的基因表达和细胞通讯程序分化成不同滋养层细胞。与当前其他可用的体外模型相比,研究者开发的sTO是更理想的体外研究模型。
② 使用空间转录组技术定义妊娠中期猪母胎界面上滋养层原位转录组图谱,无需依赖传统标志,揭示了猪子宫和胎盘的新marker,可用于精准定义猪母胎界面组织学结构;数据还包含以往未分析到的腺窝区(areola)和交界区,定义出3种腺窝细胞亚群,例如主要位于胎盘间质附近而不明显与交界区直接接触的Areola-1。总之,该图谱为后续猪生殖研究提供了基础参考。
③ 空间数据可用于注释sTO单细胞转录组数据中的细胞类型,进一步分析发现sTO涵盖了猪胎盘中滋养层细胞群的发育和功能差异,sTO和胎盘组织具有相同保守的关键信号通路。此外,由于sTO中有更多增殖干细胞,因而仅在sTO单细胞数据中观察到增殖干细胞与其他滋养层间存在互作。总之,这些凸显了sTO在研究猪胎盘发育中的用途。

图2-空间转录组学解析猪母胎界面的全局表达情况
3.猪窦卵泡的单细胞图谱
 英文标题:Deciphering Cellular Heterogeneity and Communication Patterns in Porcine Antral Follicles by Single-Cell RNA Sequencing
英文标题:Deciphering Cellular Heterogeneity and Communication Patterns in Porcine Antral Follicles by Single-Cell RNA Sequencing
发表期刊:Animals
发布时间:2023-09
DOI:10.3390/ani13193019
实验设计时空部分:单细胞转录组:D210母猪(取样前48h内注射5 IU PMSG)窦卵泡(n=2)。
研究内容总结:
① 单细胞数据揭示了猪窦卵泡内细胞的显著异质性,特别是颗粒细胞,研究者首次在猪中确认壁颗粒细胞(mGC)和卵丘细胞(nGC)存在不同亚群,例如mGC1亚群在激素信号转导中起到重要作用,而mGC2主要负责雌激素合成,cGC2负责糖酵解和卵丘扩张,cGC1亚群具有mGC和cGC两种颗粒细胞特征,表明卵泡内存在多种状态和功能的细胞。
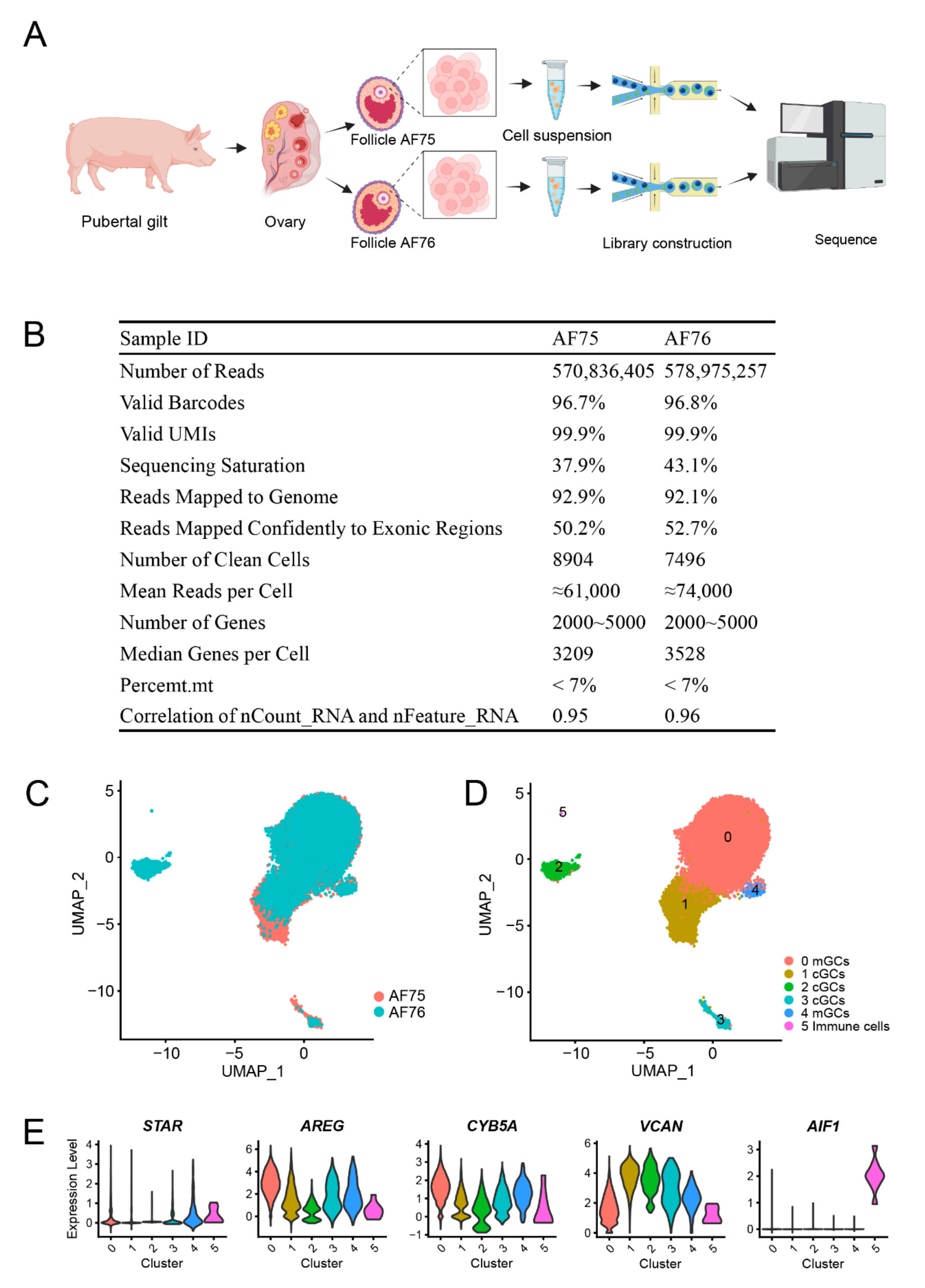
图3-猪窦状卵泡中细胞的降维聚类结果
发育方向
4.猪皮肤早期发育的时空图谱

英文标题:Integrating Single-Cell and Spatial Transcriptomics Reveals Heterogeneity of Early Pig Skin Development and aSubpopulation with Hair Placode Formation
发表期刊:Advanced Science
影响因子:14.3
发布时间:2024-04
DOI:10.1002/advs.202306703
实验设计时空部分:
单细胞转录组,E37胚胎(n=1,未知U),E41&E52&E85胚胎(每时期n=2,同窝有毛N、无毛H各1)。
空间转录组,E37胚胎(n=1),E41&E52&E85胚胎(每时期n=2,同窝有毛N、无毛H各1)。
研究内容总结:
① 单细胞数据分析得到7种主要细胞类型,空间转录组数据分析得到6种主要细胞类型,包括免疫细胞、内皮细胞、周细胞、施旺细胞等,且不同类型细胞空间分布与已知的皮肤组织解剖结构相一致,相关性分析表明单细胞数据和空间数据中鉴定出的细胞类型一致性较高。
② 联合已发表的人、小鼠皮肤单细胞数据分析,发现猪表皮细胞、免疫细胞以及周细胞表达更多保守的特异性标志基因,这些基因也与人类皮肤疾病相关,表明与小鼠相比,猪皮肤或许是一种更合适的人皮肤疾病研究模型。
③ 表皮细胞簇进一步聚类得到9种亚型,OGN+/UCHL1+ 细胞主要在E37U中存在,毛囊间表皮(IFE)基底层细胞与祖细胞从E41到E52表现出增加趋势。拟时序分析结果显示存在两种分化轨迹,OGN+/UCHL1+ 细胞—>IFE基底层细胞和真皮细胞前体(pre-DC)、OGN+/UCHL1+ 细胞—>成熟毛囊基底(Pc)发育和毛囊(HF)及角质细胞分化。真皮成纤维细胞簇进一步聚类得到乳头状成纤维细胞和网状成纤维细胞,进一步分析在E37U中鉴定出成纤维祖细胞。
④ 有毛猪中Pc的形成时期为E37-E41,无毛猪中缺乏Pc细胞。CytoTRACE、逆时序分析等结果表明,无毛猪OGN+/UCHL1+ 细胞增殖和迁移异常导致Pc不能正常形成,BMP和TGFβ是引起OGN+/UCHL1+ 细胞形成Pc的首个信号通路。
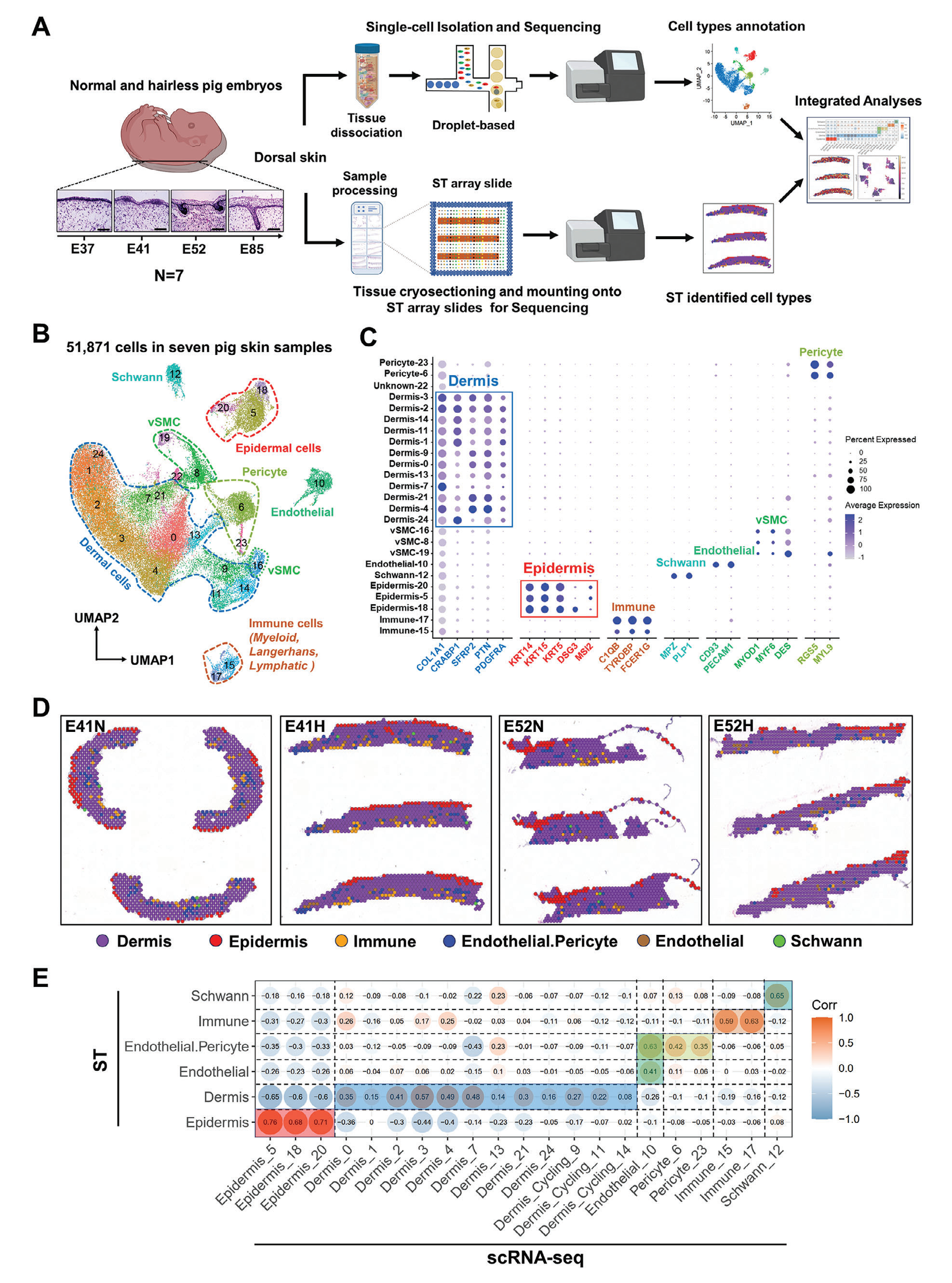
图4-ST和scRNA-seq鉴定的常见细胞类型的转录组之间具有高度一致性
5.猪出生后肝脏发育的单细胞动态图谱

英文标题:Single-cell dynamics of liver development in postnatal pigs
发表期刊:Science Bulletin
影响因子:18.8
发布时间:2023-09
DOI:10.1016/j.scib.2023.09.021
实验设计时空部分:
单细胞转录组,出生后不同胎龄猪肝脏,D30(n = 3),D42 (n = 3),D150(n = 1),D730(n = 2)。
单细胞核ATAC,D240(n=1)。
研究内容总结:
① 构建迄今最全面的出生后猪肝脏单细胞发育图谱,涵盖断奶前(30天)、断奶后(42天)、生长高峰(150天)和成年阶段(730天)这四个生长发育重要阶段,数据涵盖单细胞转录组、单细胞核转录组以及单细胞ATAC数据,共鉴定到23种细胞类型,包括肝脏中的三种稀有细胞类型,浆细胞样树突状细胞(pDCs),CAVIN3+IGF2+内皮细胞和EBF1+成纤维细胞。
② 发现断奶前仔猪和成年猪脂肪酸合成的差异,拟时序分析鉴定出5693个基因在三个发育阶段表现出显著表达水平变化,进一步分析发现33个阶段特异性转录因子,例如D30富集参与调节出生后肝细胞成熟的转录因子EZH2,D42富集参与调节昼夜节律的CLOCK,还首次鉴定出成年猪肝窦内皮特异性的转录因子LUAP2。通路富集分析结果显示不同发育阶段肝窦内皮细胞富集的通路不同,D40是免疫相关通路富集,D730中主要是代谢相关通路基因表达上调。
③ 猪D30免疫细胞主要是NK(自然杀伤细胞)和T细胞,以往有报道表明新生小鼠免疫系统重髓系细胞占比更大,出生D30猪肝脏免疫系统可能发生了从髓系细胞到淋巴系细胞的免疫系统转变。此外,猪trNK(组织驻留自然杀伤细胞)具有与人类相似的转录因子表达特征,或表明猪可以作为研究人trNK的理想模型。
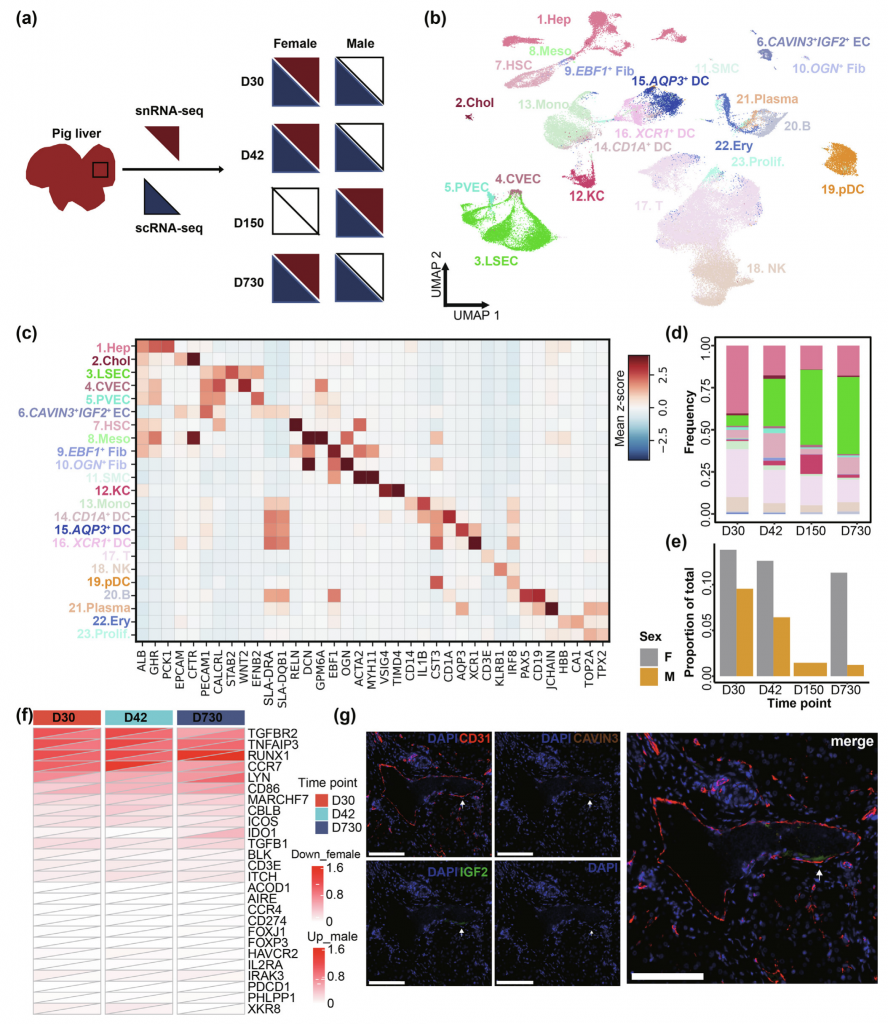
图5-单细胞RNA测序(scRNA-seq)和单核RNA测序(snRNA-seq)鉴定发育中肝脏细胞类型
免疫方向
6.猪肾异种移植排异的时空图谱

英文标题:Spatiotemporal immune atlas of a clinicalgrade gene-edited pig-to-human kidney xenotransplant
发表期刊:Nature Communications
影响因子:14.7
发布时间:2024-04
DOI:10.1038/s41467-024-47454-7
实验设计时空部分:
单细胞核转录组,移植前猪肾穿刺组织,移植后24h/72h/74h猪肾穿刺组织(n=4)。单细胞转录组,移植74h后切除的肾组织CD45+细胞(n=1);
空间转录组,移植前猪肾穿刺组织,移植后24h/72h/74h猪肾穿刺组织(n=4)。
研究内容总结:
① 基因编辑猪肾移植给脑死亡且双肾切除患者。数据分析结果显示,未在异种移植后的猪肾组织中发现急性细胞排异或IgM/IgG/配体蛋白结合的证据,但发现急性肾小管坏死和病因不明的血栓性微血管病变。
② 移植后猪肾中髓系细胞是人和猪肾中检测到的最多的免疫细胞,移植3天内人B细胞和T淋巴细胞很少检测到,3天后检测到的人免疫细胞增多但丰度远小于猪免疫细胞。
③ 移植3天后发现人类中性粒细胞和单核细胞主要与猪内皮细胞共定位,人巨噬细胞主要与猪基质细胞共定位,表明人免疫细胞对猪肾皮质浸润有限。
④ 移植猪肾中人和猪巨噬细胞更倾向于激活抗炎症基因表达。
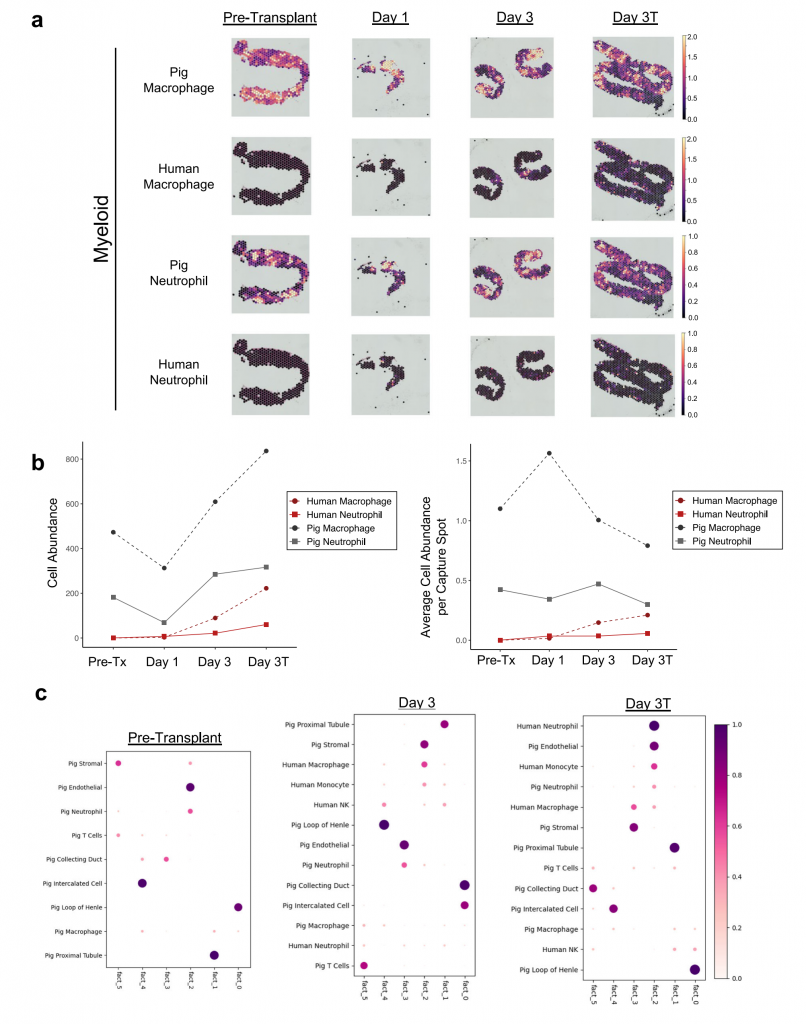
图6-人髓系细胞对猪肾异种移植的有限浸润
7.猪空肠免疫细胞单细胞图谱
?
英文标题:Single-Cell Transcriptional Analysis of Lamina Propria Lymphocytes in the Jejunum Reveals Innate Lymphoid Celllike Cells in Pigs
发表期刊:The Journal of Immunology
发布时间:2024-01
DOI:10.4049/jimmunol.2300463
实验设计时空部分:
单细胞转录组,4周大仔猪,空肠固有层淋巴细胞(n=3),空肠先天淋巴样细胞(n=3)。
研究内容总结:
② 猪空肠ILC标志基因与人基因相似,包括IL-23R、AHR、NCR2等。此外,研究者发现ILC3可能分化成ILC2、ILC1和NK细胞。ILC3亚群种,ILC3b没有明显高表达基因,是ILC亚群中具有更高转分化可塑性的亚群,IKZF1和TGFB1可能与该过程有关。
③ 猪ILC3表达TAC3基因,该基因编码蛋白的受体是NK3R,可以促进释放促性腺激素释放激素,继而促进性激素释放,因此TAC3在促性腺激素轴上起到重要作用,因而可能存在肠/性腺轴,暗示猪肠道ILC3或调控性腺发育。
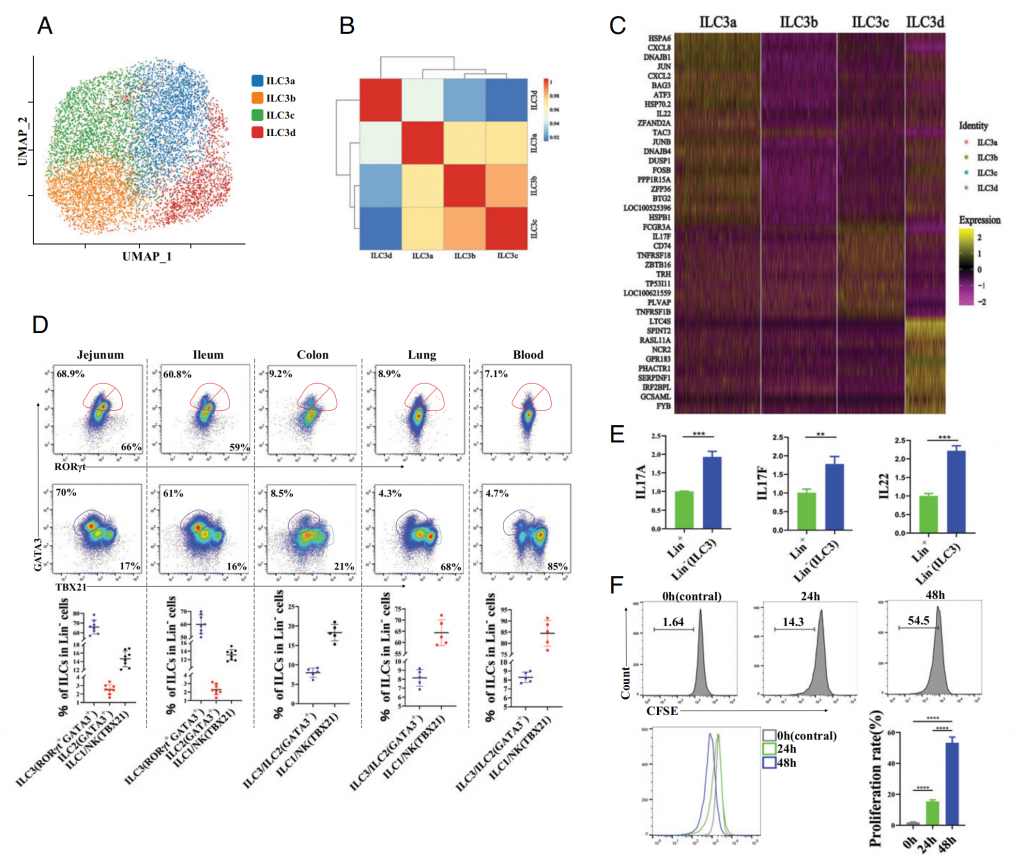
图7-猪空肠中lLC3s的分型研究
8.感染PEDV仔猪的空肠单细胞图谱
?
英文标题:Identification of Cell Types and Transcriptome Landscapes of Porcine Epidemic Diarrhea VirusInfected Porcine Small Intestine Using Single-Cell RNA Sequencing
发表期刊:The Journal of Immunology
发布时间:2023-02
DOI:10.4049/jimmunol.2101216
实验设计时空部分:
单细胞转录组,口服2ml PEDV-24h的3天大仔猪(n=1,4只猪样本混合),口服对照液体-24h的3天大仔猪(n=1,4只猪样本混合)
研究内容总结:
① 首次绘制感染PEDV(猪流行性腹泻病毒)的仔猪小肠单细胞图谱,使用人小肠细胞类型marker鉴定出12种细胞类型,发现猪小肠tuft细胞新特异性标志基因DNAH11,结果表明多数人小肠特异性marker也可以用到猪研究中。此外,猪小肠Th17细胞(3和9簇)特异性高表达IL17A、IL7F和IL22,但不高表达T细胞代表性CD3,这可能与猪T细胞分化有关。
② 抗菌肽(AMP)相关基因分析结果显示,仅DEFB115和REG3G在仔猪空肠部分的肠细胞中最为丰富,PEDV感染会导致REG3G显著上调。REG3G表达与IL33、MyD88、STAT3等相关,在体外实验中发现感染PEDV后IPEC-J2细胞IL33表达水平以及STAT3磷酸化水平显著增加,表明IL33-STAT3信号通路可能在PEDV感染诱导的REG2G表达中起到重要作用。
③ 功能富集分析结果显示,病毒感染导杯状细胞、tuft细胞和肠内分泌细胞中紧密连接和粘附连接通路水平显著降低,体外实验确认PEDV感染的IPEC-J2细胞中,紧密连接通路相关基因表达显著降低,但感染晚期粘附连接通路相关基因转录和蛋白质水平表达显著增加,这可能是由于不同肠细胞类型对PEDV感染的不同响应导致的。冠状病毒受体分析结果表明,猪小肠上皮细胞高表达多种不同的冠状面病毒受体,这一发现支持猪易受冠状病毒感染并表现感染相关肠道症状。
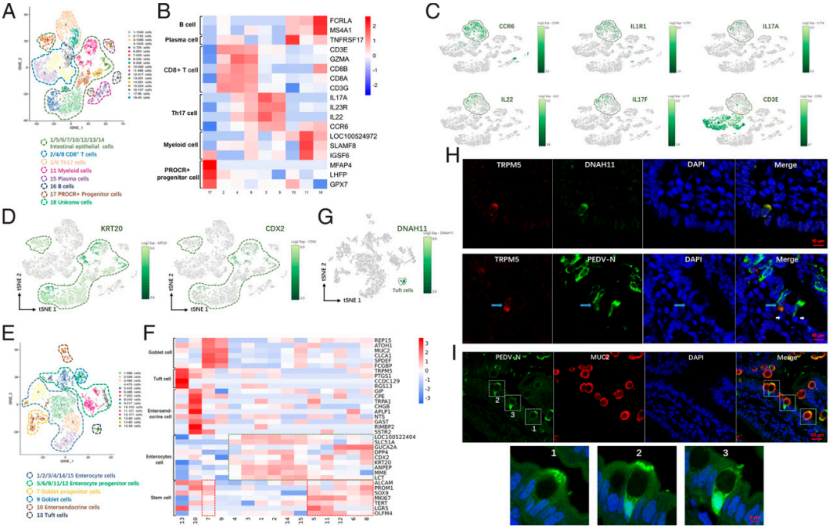
图8-猪小肠空肠段细胞类型的测定
同源器官比较
9.脊椎动物肺单细胞图谱

英文标题:Origin and stepwise evolution of vertebrate lungs
发表期刊:Nature ecology & evolution
影响因子:14.1
发布时间:2025-2
DOI:10.1038/s41559-025-02642-6
实验设计时空部分:
单细胞转录组测序:
塞内加尔多鳍鱼,肺(n=2),脑/食管/鳃/心脏/肠/肌肉/胃(各器官,n=1);
非洲肺鱼,肺(n=2),脑/食管/鳃/心脏/肠/肾/肌肉/皮肤/胃(各器官,n=1);
条纹斑竹鲨,壶腹/鱼鳍/心脏/肠/胰腺/鳃/牙(各器官,n=3),脑/食管/肾(各器官,n=2),脾脏(n=6),眼睛(n=1);鸡肺,E6/E7/P3(各时期,n=1);
非洲牛蛙肺(n=2);鬃狮蜥肺(n=1)。
人/小鼠/大鼠/猪的肺数据使用已有的单细胞转录组测序数据。
百迈客生物为塞内加尔多鳍鱼和非洲肺鱼除肺以外的组织,提供了百创DG1000单细胞转录组测序服务。
研究内容总结:
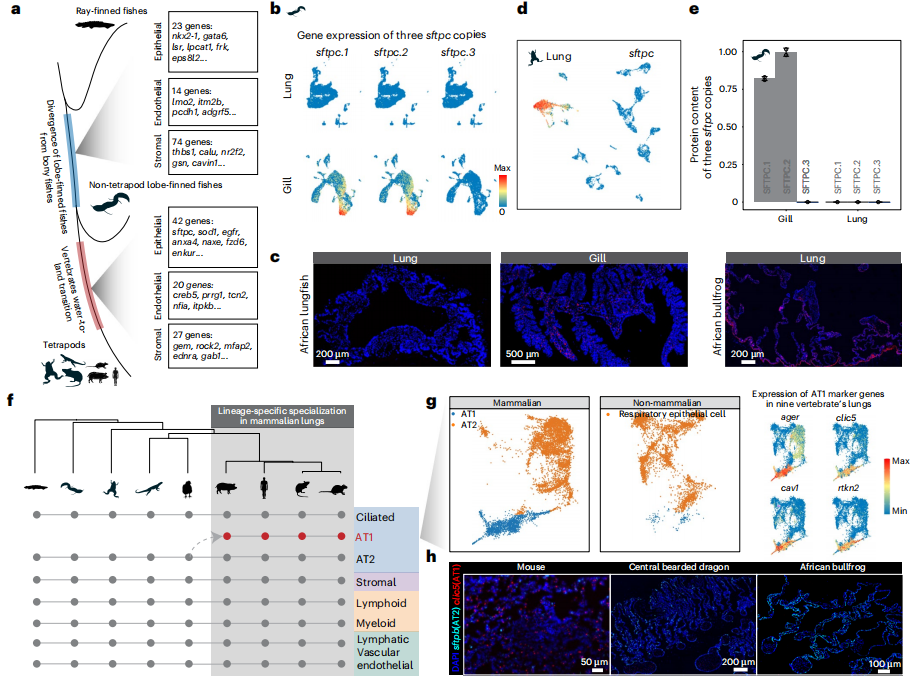
① 使用单细胞转录组测序分析9种动物的成体/胚胎肺组织及其他组织,发现软骨鱼具有多个肺发育所必须得遗传组分,包括肺特异性基因,但不同物种中这些基因的表达模式和功能可能有差异,表明软骨鱼距离拥有肺在“进化上只差一步之遥”;软骨鱼食管和胃中,少量细胞共表达对呼吸脊椎动物肺功能十分重要的sftpb和abca3基因,暗示颌类脊椎动物最近共同祖先(LCA)经历显著的演化变化,不仅发育出重要特征如颌和成对附件,还为肺最终出现奠定基础。
② 许多保守的非编码组分(CNE)来源于颌类脊椎动物祖先,暗示肺的遗传基础可能在脊椎动物演化很早就出现,但无肺蝾螈中缺失的CNE与其促肺活性无关,表明这些组分可能还具有除肺发育以外的多种功能;硬骨鱼祖先来源的CNE在无肺蝾螈表现出更高的丢失率,也反映出这些CNE具有显著的肺功能特异性,强调了复杂器官起源中调控组分演化的重要性。这些证据暗示肺起源的两个阶段过程,最开始颌类脊椎动物LCA出现基础的肺相关遗传组分,随后谱系演化出更特异性的肺增强子产生硬骨鱼;功能完全的肺可能在软骨鱼和硬骨鱼谱系分开后演化而来。
③ 全基因组复制对肺演化很重要,1866个肺相关直系同源基因中有776个是脊椎动物两轮全基因组复制(2R-WGD)的产物;哺乳动物谱系特异的基因复制也十分重要,sfta2-/-小鼠表现出明显的呼吸疾病,包括显著的炎症。
④ 研究成果支持了两个关于复杂器官的前期假设。首先,肺进化是一个逐步过程,与达尔文预测相一致,与眼睛和其他器官类似,肺演化似乎是随时间逐渐发生的。其次,反映了Jacob定律,即演化类似“修补匠”,使用已有的遗传基础,包括招募、征用已经存在的基因和调控组分。总之,这些结果表明调控网络的修改对肺的起源和演化是十分重要的,新基因或基因重复的出现提供了基础材料,即使这些基因并不会立刻发挥作用。
10.野猪/莱芜猪/杜洛克猪新生骨骼肌单细胞图谱
 英文标题:Single-Cell RNA-Sequencing Provides Insight into Skeletal Muscle Evolution during the Selection of Muscle Characteristics
英文标题:Single-Cell RNA-Sequencing Provides Insight into Skeletal Muscle Evolution during the Selection of Muscle Characteristics
发表期刊:Advanced Science
影响因子:14.3
发布时间:2023-10
研究内容总结:
① 使用单细胞转录组测序技术绘制了野猪、莱芜猪和杜洛克猪新生骨骼肌驻留细胞图谱,鉴定出9种细胞类型,包括成肌细胞、肌细胞、卫星细胞等,定义两种新亚型,MT丰富FAP(?bro-adipogenic progenitors)以及肌细胞样FAP。
② 与不同物种的胎儿和成体骨骼肌相比,猪新生骨骼肌细胞组成类型更丰富。例如,猪新生骨骼肌卫星细胞不仅包含卫星干细胞(PAX7+),还包括两个有不同肌源性潜能的亚群(HES1+和TRIB1+卫星细胞);少有研究可解答骨骼肌中FAP的异质性,但本研究发现4种FAP亚群。与人、小鼠骨骼肌数据联合分析,发现猪骨骼肌驻留细胞的通用marker和物种特异性的marker。
③ 猪新生骨骼肌中发现增殖分化活性状态的干性样细胞,如pro-NK/T、间充质干细胞(MSC)、间质细胞等,且MSC和FAP间存在一群具有典型标志基因如CD73、CD90和PDGFRA的连续态细胞亚群。此外,拟时序分析揭示杜洛克猪新生骨骼肌中的成肌谱系干细胞处于初始阶段,野猪的成肌谱系已处于分化末期和成熟期,莱芜猪位于中间态。
④ 不同品种猪具有不同骨骼肌表型,它们骨骼肌驻留细胞谱系存在一定差异。与家猪相比,野猪缺少两种FAP亚群,但存在THY1+卫星细胞;发现品种特异性细胞类型,例如莱芜猪具有COL13A1+ 腱细胞;与莱芜猪和野猪相比,杜洛克猪新生肌肉中具有更多增殖的前体脂肪细胞,或意味杜洛克猪未来选育后可积累更高的IMF(肌内脂肪)。
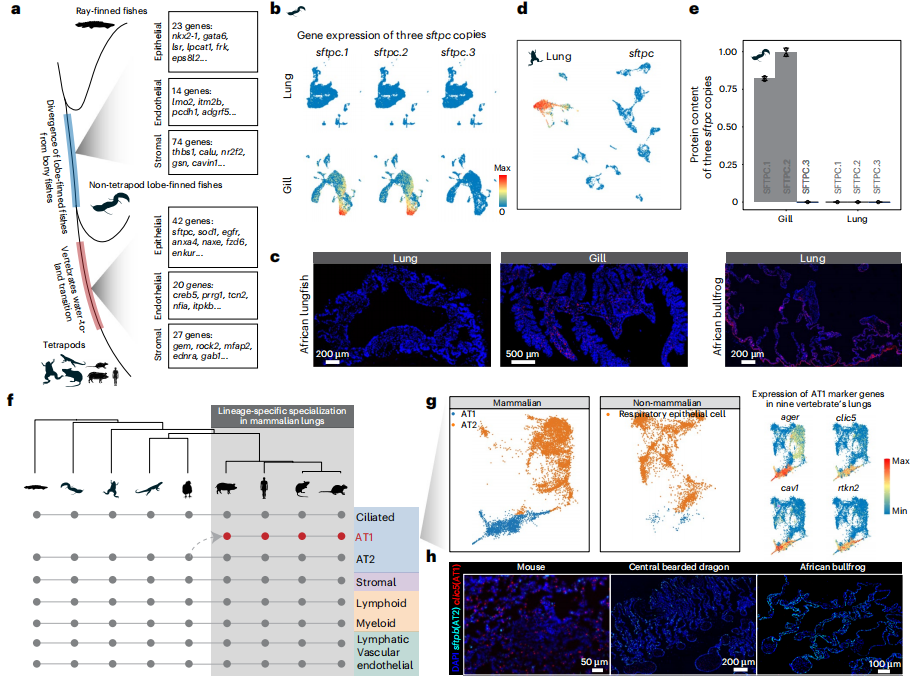
图9-野猪、莱芜猪和杜洛克猪骨骼肌细胞的单细胞转录谱分析
11.人/小鼠/大鼠/猪胃窦跨物种比较单细胞图谱

英文标题:Cross-species single-cell transcriptomic analysis of animal gastric antrum reveals intense porcine mucosal immunity
发表期刊:Cell Regeneration
发布时间:2023-08
DOI:10.1186/s13619-023-00171-w
实验设计时空部分:单细胞转录组,人(n=4),小鼠(n=3),大鼠(n=3),猪(n=3)。
研究内容总结:
① 使用单细胞转录组测序技术构建人、猪、大鼠和小鼠的胃窦单细胞转录组图谱,鉴定出9种类型的细胞,包括小凹黏膜细胞、小凹祖细胞、基底腺粘液细胞等。绝大多数类型的细胞存在于两个或者多个物种中,F3和CLCA1低表达水平的祖细胞仅在人类和猪的胃窦上皮中发现,高表达F3的基底粘液腺细胞仅在猪胃窦上皮中发现,通路富集分析表明F3+细胞类群可能与细胞迁移、细胞增殖以及蛋白稳定维持相关。
② 功能富集分析结果表明,人的胃窦上皮高表达金属离子稳态相关基因,猪的胃窦上皮高表达免疫相关基因,大鼠和小鼠的胃窦上皮高表达脂代谢相关基因,这种差异可能是由于饮食习惯导致的。猪胃窦上皮类器官bulk RNA-seq数据也确认这一发现,进一步的猪胃窦上皮细胞类器官体外实验结果表明,TNFα能够特异性地上调T细胞和B细胞活化相关基因,这些结果表明,正常生理状态下猪胃窦上皮细胞具有强免疫能力,可能与其复杂饮食习惯和居住环境有关。
③ 进一步分析人和猪胃窦中的免疫细胞,发现人胃窦免疫细胞高表达B细胞/T细胞激活和功能相关基因,而猪胃窦显著高表达B细胞/T细胞细胞增殖相关基因;细胞通讯分析结果显示,人胃窦中上皮细胞和基质细胞间高表达或特异性表达免疫细胞产生、成熟、维持和功能相关受配体对,而猪中主要是与上皮细胞生长分化、抗炎症和抗菌、免疫细胞增殖相关。
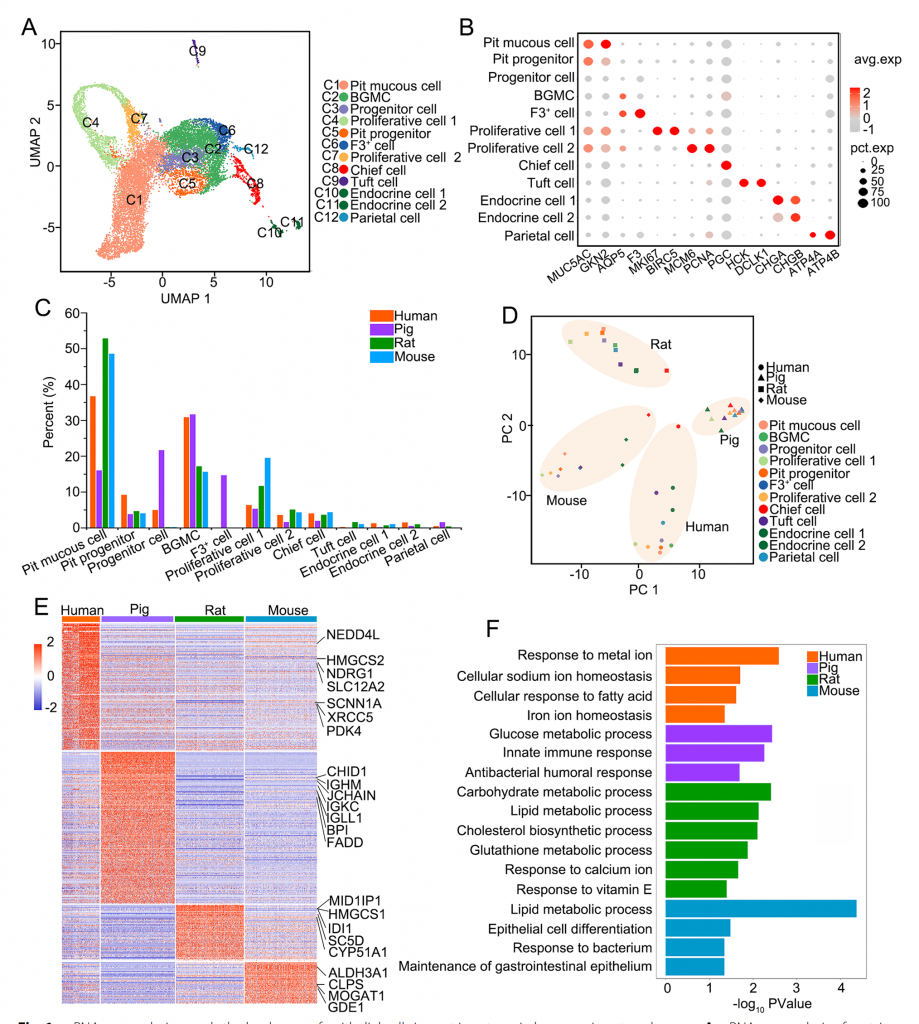
图10-scRNA-seq分析揭示了人、猪大鼠和小鼠胃窦细胞组成及基因表达谱
基础图谱
12.猪器官全景单细胞图谱

英文标题:Endothelial cell heterogeneity and microglia regulons revealed by a pig cell landscape at single-cell level
发表期刊:Nature Communications
影响因子:14.7
发布时间:2022-06
DOI:10.1038/s41467-022-31388-z
实验设计时空部分:
单细胞转录组,6个月大猪,肝(n=1),血液PBMC(n=1),视网膜(n=1),脾脏(n=1),肠道(n=1),肺(n=1),脂肪组织(n=2)。
单细胞核转录组,6个月大猪,脑(n=9),视网膜(n=1),肾脏(n=1),心脏(n=1),脾脏(n=1),肝脏(n=1),肺(n=1)。
研究内容总结:
① 使用单细胞转录组测序及单细胞核转录组测序,构建首个家猪多器官单细胞图谱,得到234种降维聚类簇,鉴定出58种细胞类型及其相关的显著富集标志基因,搭建了可视化家猪单细胞转录组数据库(Pig Single Cell Atlas Database)。
② 对血管内皮细胞数据进一步分析,鉴定出21种具有特异表达特征和功能的血管内皮细胞类型,包括脂肪组织中依赖于TGF-b2信号通路内皮-间充质转化亚型;人/猪肝脏、肾脏和心脏组织中,内皮细胞主要通过VEGF、PDGF,TGF-β和BMP通路与其他细胞类型互作,但不同细胞类型的互作通路有差异,例如猪内皮细胞可与肝脏免疫细胞、心脏所有细胞细胞类型通过PDGF交流,但在肾脏中可通过PDGF通路与内皮细胞交流的仅有足细胞。总之,这些结果表明家猪单细胞图谱为研究猪或人组织中细胞间互作提供了有参考价值的基础数据。
③ 对家猪、人、小鼠、猴、仓鼠、栗鼠、鼹鼠等13个物种的大脑小胶质细胞单细胞转录组数据进行分析,发现1590个保守的转录组因子(TF)靶向对,其中MEF2C、SPI1、IRF8、ZFP36L1在13个物种的小胶质细胞中均高表达,这些结果表明家猪单细胞图谱为研究不同物种小胶质细胞保守和差异的遗传调控网络提供了基础数据,对未来脑小胶质细胞功能研究发展具有重要意义。
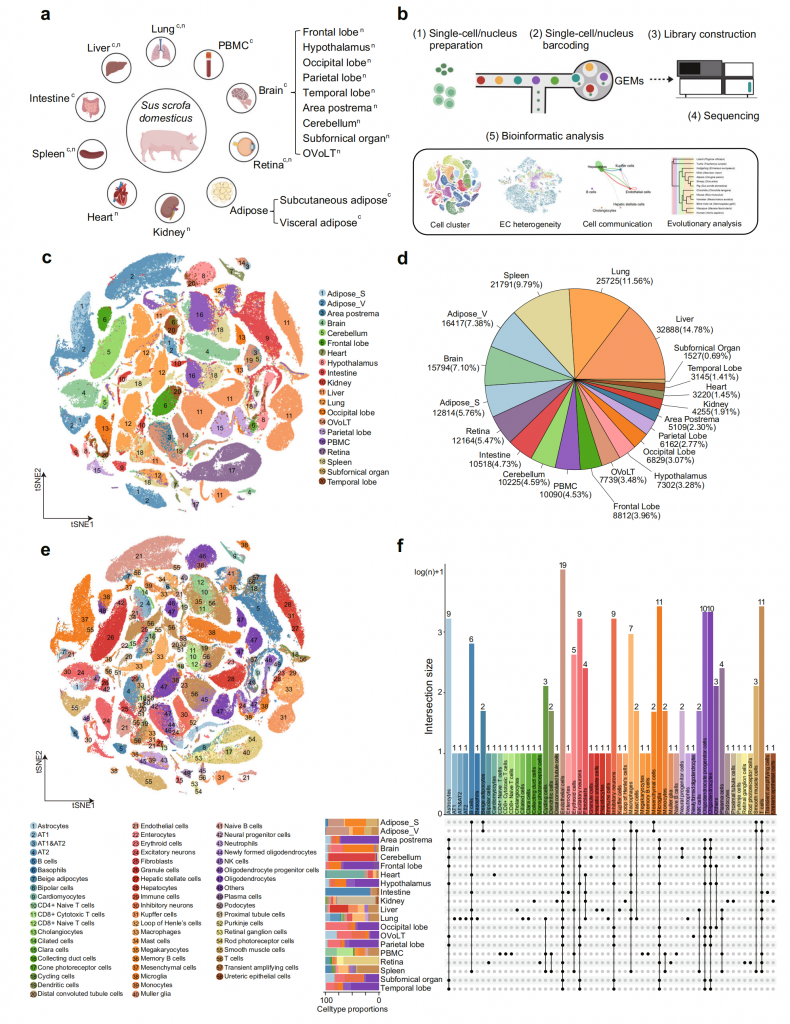
图11-猪20种组织单细胞图谱
从以上文章可以看到,猪相关研究除了养殖、繁育、品种优化、营养学、表型性状、遗传演化等方面,生殖、发育、衰老、损伤与修复、异种移植、神经学等方向研究成果也具有较高参考和转化价值。未来,可能会出现猪睾丸、胚胎发育、心血管组织、脑组织、疾病模型、异种移植/同种异体移植、鼻嗅觉、舌味觉、免疫系统等方向的研究成果。
Ps:关注时空组学在猪领域研究请联系当地业务经理获取原文~
1. Ge W, Niu YL, et al. Spatiotemporal dynamics of early oogenesis in pigs. Genome Biol. 2025 Jan 2;26(1):2.
2. Cole R. McCutcheon, et al. Defining Cellular Diversity at the Swine Maternal-Fetal Interface Using Spatial Transcriptomics and Organoids. bioRxiv. 2024.
3. Chen N, et al. Deciphering Cellular Heterogeneity and Communication Patterns in Porcine Antral Follicles by Single-Cell RNA Sequencing. Animals (Basel). 2023 Sep 26;13(19):3019.
4. Wang Y, et al. Integrating Single-Cell and Spatial Transcriptomics Reveals Heterogeneity of Early Pig Skin Development and a Subpopulation with Hair Placode Formation. Adv Sci (Weinh). 2024 May;11(20):e2306703.
5. Rao L, et al. Single-cell dynamics of liver development in postnatal pigs. Sci Bull (Beijing). 2023 Nov 15;68(21):2583-2597.
6. Cheung MD, et al. Spatiotemporal immune atlas of a clinical-grade gene-edited pig-to-human kidney xenotransplant. Nat Commun. 2024 Apr 11;15(1):3140.
7. Wang J, et al. Single-Cell Transcriptional Analysis of Lamina Propria Lymphocytes in the Jejunum Reveals Innate Lymphoid Cell-like Cells in Pigs. J Immunol. 2024 Jan 1;212(1):130-142.
8. Fan B, et al. Identification of Cell Types and Transcriptome Landscapes of Porcine Epidemic Diarrhea Virus-Infected Porcine Small Intestine Using Single-Cell RNA Sequencing. J Immunol. 2023 Feb 1;210(3):271-282.
9. Li, Y., et al. Origin and stepwise evolution of vertebrate lungs. Nat Ecol Evol (2025).
10. Xu D, et al. Single-Cell RNA-Sequencing Provides Insight into Skeletal Muscle Evolution during the Selection of Muscle Characteristics. Adv Sci (Weinh). 2023 Dec;10(35):e2305080.
11. Wang X, et al. Cross-species single-cell transcriptomic analysis of animal gastric antrum reveals intense porcine mucosal immunity. Cell Regen. 2023 Aug 1;12(1):27.
12. Wang F, et al. Endothelial cell heterogeneity and microglia regulons revealed by a pig cell landscape at single-cell level. Nat Commun. 2022 Jun 24;13(1):3620.
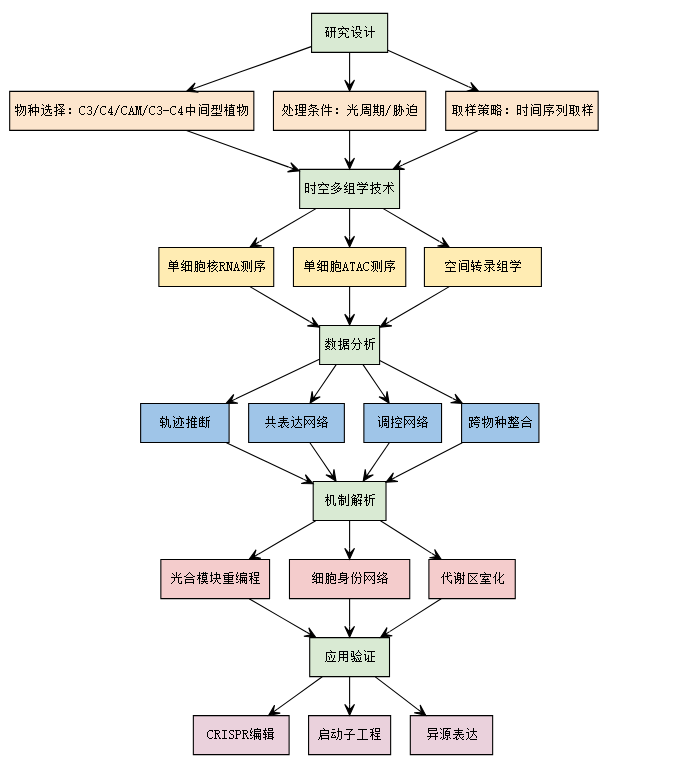
]]>近年来,光合作用作为植物生命活动的核心环节,与粮食安全、能源开发及气候变化等全球性挑战密切相关,备受科学界和行业的高度关注。时空组学技术是近年来比较火热的技术之一,在植物领域的应用广泛且深入,该技术通过同时获取细胞的空间位置信息和基因表达数据,为理解植物组织生长发育、生理生化、抗逆应激、生物进化等多个方面提供了重要的研究手段。
于是,我问DeepSeek:植物如何利用时空组学进行光合作用研究?
 植物利用时空组学(Spatio-Temporomics)研究光合作用,主要通过整合空间组学(空间分辨的分子数据)和时间组学(动态变化的分子数据),揭示光合作用相关基因、蛋白质、代谢物等在时间和空间上的协同调控机制。以下是具体研究方向和技术的应用:1.空间组学解析光合作用的细胞/组织异质性
植物利用时空组学(Spatio-Temporomics)研究光合作用,主要通过整合空间组学(空间分辨的分子数据)和时间组学(动态变化的分子数据),揭示光合作用相关基因、蛋白质、代谢物等在时间和空间上的协同调控机制。以下是具体研究方向和技术的应用:1.空间组学解析光合作用的细胞/组织异质性
- 空间转录组学:
利用单细胞或空间分辨转录组技术(如10x Genomics Visium、MERFISH),定位光合作用相关基因(如编码光系统蛋白的基因、卡尔文循环酶基因)在叶片不同细胞类型(叶肉细胞、维管束鞘细胞)或不同组织区域的表达差异。例如,C4植物中光合基因在叶肉细胞和维管束鞘细胞中的空间特异性表达。
- 空间蛋白质组学:
通过质谱成像(MALDI-MSI)或荧光标记技术,研究光合作用关键蛋白(如Rubisco、PSII复合体)在叶绿体基质、类囊体膜等亚细胞结构中的分布,以及光强变化对蛋白定位的影响。
- 空间代谢组学:
分析光合中间产物(如ATP、NADPH、蔗糖)在叶片不同区域的动态积累,揭示光合同化产物(如淀粉、糖)的运输与分配机制。
2.时间组学揭示光合作用的动态调控
- 昼夜节律与光响应:
通过时间序列转录组、蛋白质组数据,研究光合作用基因(如LHCB、PIFs)在昼夜周期中的表达波动,以及光信号(如红光、蓝光)如何通过生物钟调控光合效率。
- 发育阶段动态:
比较幼苗、成熟叶、衰老叶中光合相关基因的时序表达模式,揭示叶绿体发育(如原质体分化)和衰老过程中光合能力的动态变化。
- 环境胁迫响应:
分析高温、干旱或高光胁迫下,植物光合作用相关基因和代谢物的短期(分钟级)和长期(数天)响应,例如光保护机制(非光化学淬灭,NPQ)的动态调控。
3.时空整合解析光合作用的协同网络
- 多组学整合:
结合空间转录组、蛋白质组和代谢组数据,构建光合作用基因-酶-代谢物的时空调控网络。例如,光合同化产物(如蔗糖)的输出如何与维管组织发育相关联。
- 细胞间通讯研究:
利用空间组学数据,分析叶肉细胞与维管束鞘细胞之间的代谢物交换(如C4植物的CO2浓缩机制),或共生微生物(如固氮菌)如何影响宿主光合作用。
- 3D时空建模:
通过计算模型模拟叶片中光梯度、CO2扩散与光合基因表达的空间耦合关系,预测最优光合效率的叶片结构。
4.应用场景与案例
- C3与C4植物比较:
时空组学可揭示C4植物光合细胞分工(Kranz结构)的进化机制,例如PEP羧化酶在维管束鞘细胞中的特异性表达。
- 作物改良:
通过筛选光合效率时空差异的基因(如调控气孔开闭的基因),设计高光效作物品种。
- 极端环境适应:
研究荒漠植物(如仙人掌)如何在干旱条件下时空调控光合相关基因,减少水分流失。
5.技术挑战与未来方向
- 技术限制:
当前空间组学分辨率(单细胞/亚细胞级别)和通量仍需提升,尤其是叶绿体内分子动态的实时监测。
- C3与C4植物比较:
跨尺度(分子-细胞-组织)和多组学数据的整合分析需要更强大的算法支持。
- 活体动态监测:
开发非侵入式成像技术(如荧光报告系统),实时追踪光合作用相关分子的时空动态。
DeepSeek提到的当前空间组学分辨率(单细胞/亚细胞级别)和通量的限制,百迈客生物已经进行了优化提升,推出了百创S3000空间转录组芯片(捕获区面积:6.8*6.8mm2,相邻两个捕获位点的中心距为3.5μm)。该芯片具有高基因捕获效率,搭配植物多尺度细胞分割技术,部分植物组织单个细胞中位基因数可达1000+,基因捕获能力媲美单细胞测序。

关于应用方向场景案例,DeepSeek究竟说的对不对?
我们还需要结合已发表的文献看一看,于是小编又下载盘点了7篇植物光合作用方向的时空组学文章,这些成果发表期刊有Nature(IF=50.5)与预印本系统bioRxiv。研究的物种涉及水稻、高粱、玉米、狗尾草、黍、冰叶日中花、Urochloa fusca、堇娘芥等,涉及组织部位主要是幼苗叶片、叶原基等。
接下来,我们一起来看看植物光合作用方向的时空组学应用进展吧!
1.祖先细胞身份网络的扩展驱动C4光合作用的进化
 英文标题:Exaptation of ancestral cell-identity networks enables C4?photosynthesis发表期刊:Nature
英文标题:Exaptation of ancestral cell-identity networks enables C4?photosynthesis发表期刊:Nature
影响因子:50.5
物种样本:水稻(Oryza sativa,C3植物)、高粱(Sorghum bicolor,C4植物)
测序策略:单细胞核RNA测序、单细胞核多组学测序、高分辨率sci-RNA-seq3技术
DOI:https://doi.org/10.1038/s41586-024-08204-3
发表时间:2024.11.20
取样策略:
单细胞核转录组:水稻和高粱幼苗暗生长5天后,在光周期(12h光/12h暗)中采集0h(暗)、0.5h、1h、2h、4h、6h、8h、12h、48h共9个时间点的地上组织。总计水稻190,569个核、高粱265,701个核。

图1-水稻和高粱单细胞测序取样过程示意图
① 地球上大多数高产植物通过C4途径进行光合作用,相较于原始的C3途径,C4途径的光合效率提高了50%。维管束鞘细胞在激活光合作用中扮演了关键角色。然而,维管束鞘细胞如何执行光合调控功能尚不明确。
② 该研究通过单细胞RNA测序(sc-RNAseq)和单细胞转座酶可及性染色质测序(sc-ATACseq),揭示了C4叶片中维管束鞘细胞基因表达的变化与C3叶片中已知的顺式调控元件相关。研究发现,在C3植物水稻和C4植物高粱中,DOF motif在维管束鞘细胞中定位,并能调控光合作用的发展。在高粱中,大多数受光合作用调控的高表达基因都受到DOF motif的调控。这些转录因子在不同细胞间稳定表达,并能在C3和C4植物叶片的维管束鞘细胞中激活光合作用。
③ 该研究结果为理解复杂的C4途径进化提供了分子层面的见解,并为指导C3和C4作物的生长发育提供了理论基础。
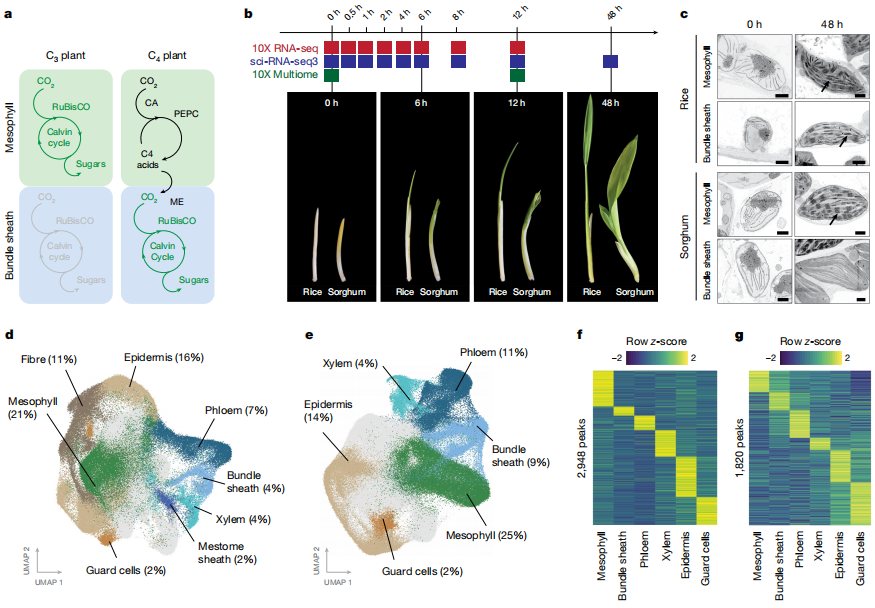
图2-水稻和高粱幼苗去黄化过程中单细胞核的基因表达和染色质可及性
2.禾本科植物单细胞分辨率下C3与C4光合作用顺式调控基础研究
 英文标题:Investigating the cis-Regulatory Basis of?C3?and?C4?Photosynthesis in Grasses at Single-Cell Resolution发表期刊:bioRxiv
英文标题:Investigating the cis-Regulatory Basis of?C3?and?C4?Photosynthesis in Grasses at Single-Cell Resolution发表期刊:bioRxiv
物种样本:C4植物:玉米(Zea mays,NADP-ME型)、高粱(Sorghum bicolor,NADP-ME型)、黍(Panicum miliaceum,NAD-ME型)、Browntop Signalgrass(Urochloa fusca,PEPCK型);对照C3植物:水稻(Oryza sativa)
测序策略:sciATAC-seq
DOI:https://doi.org/10.1101/2024.01.05.574340
发布时间:2024.01.05
取样策略:
发育阶段:C4物种取第三叶展开期叶片,C3水稻取18天龄叶片;
技术重复:每个物种设置生物学重复,总计玉米16,060核、高粱15,301核、黍7,081核、Browntop Signalgrass共19,110核、水稻5,952核。
① 尽管关于C4光合作用关键酶的研究已经有了相当多的认识,但对于在特定细胞类型中指定其表达的重要顺式调控机制(cis-regulation)的了解却少之又少。
② 该研究使用单细胞sci-ATAC-seq来鉴定与C4酶相关的特异细胞类型的可及染色质区域(ACRs),研究涵盖了五种不同的禾本科植物,包括四种C4植物和一种C3植物。其中,C4植物分属三种不同的光合亚型:玉米(Zea mays)和高粱(Sorghum bicolor)属于NADP-ME亚型;黍(Panicum miliaceum)属于NAD-ME亚型;Urochloa fusca属于PEPCK亚型;C3植物水稻(Oryza sativa)
③ 该研究绘制了所有C4植物中必需酶和各C4亚型特有酶的cis-调控图谱,并使用染色质可及性数据测量C4酶的特定细胞类型偏好。将这些数据与系统发育学相结合,揭示了物种间基因家族成员的多样化共选择,展示了C4进化的不同路径。除了启动子近端ACRs,研究发现C4基因平均每个都有两到三个远端特异性细胞类型的ACRs,这突出了C4进化的复杂性和多样性。在研究这些特异性细胞类型ACRs的进化历史时,发现即使在密切相关的物种中,也存在从保守到新颖的ACRs光谱,表明这些C4位点的顺式调控正在持续进化。
④ 该研究揭示了C4光合作用关键基因位点的顺式调控进化动态和复杂性,尤其强调了这些位点的精细化顺式调控进化。研究成果为未来进一步探索提供了重要资源,可能有助于在气候变化条件下优化C3作物的性能。
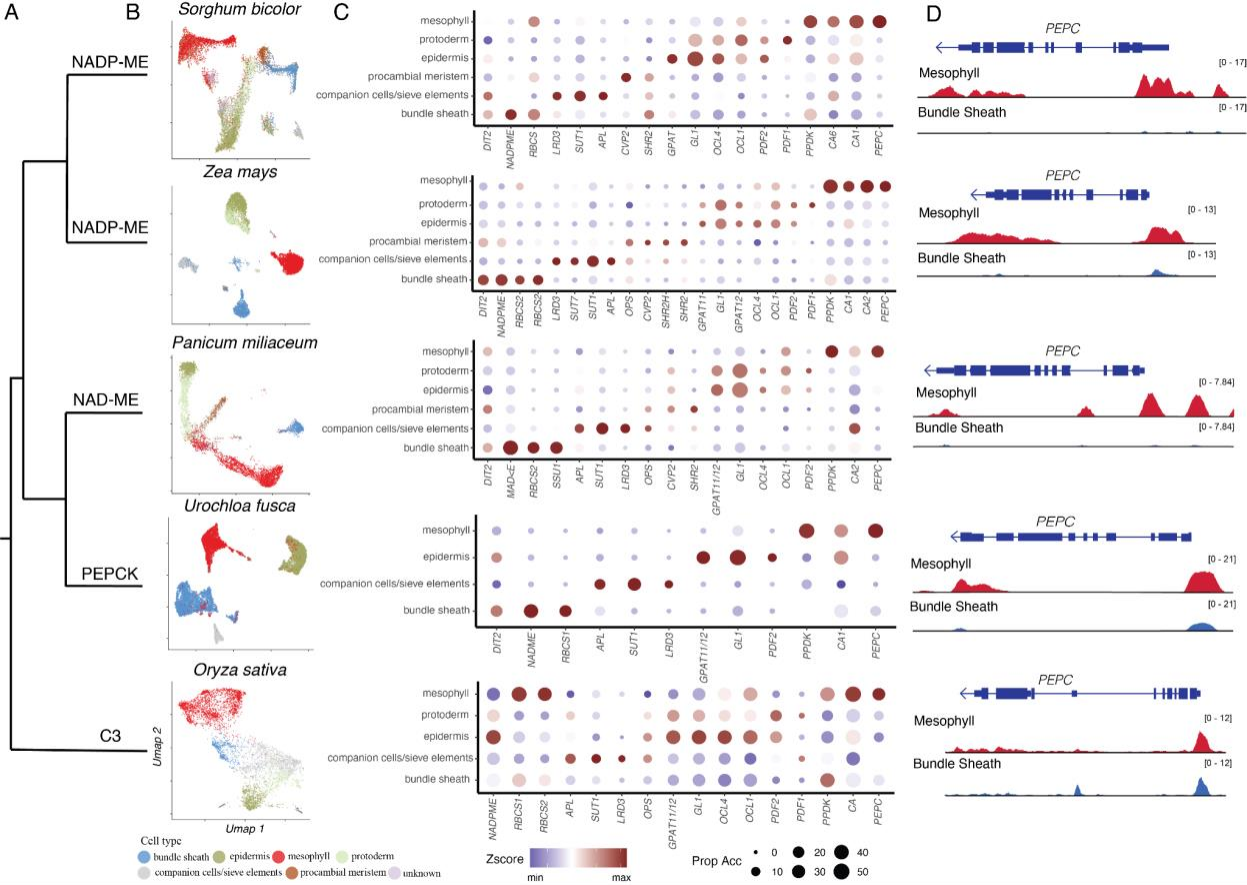
图3-在单细胞分辨率下对不同作物的细胞类型注释
3.单细胞分辨率下冰叶日中花CAM诱导的叶肉特异性昼夜动态
 英文标题:Mesophyll-Specific Circadian Dynamics of CAM Induction in the Ice Plant Unveiled by Single-Cell Transcriptomics发表期刊:bioRxiv
英文标题:Mesophyll-Specific Circadian Dynamics of CAM Induction in the Ice Plant Unveiled by Single-Cell Transcriptomics发表期刊:bioRxiv
物种样本:冰叶日中花(Mesembryanthemum crystallinum,兼性CAM植物)
测序策略:单细胞核RNA测序、Iso-Seq全长转录组测序、基因组组装
DOI:https://doi.org/10.1101/2024.01.05.574430
发布时间:2024.01.05
取样策略:
处理条件:盐胁迫组:5周龄植株经0.5M NaCl处理8天;
对照组:正常灌溉植株;
时间点:光周期(12h光/12h暗)中采集黎明(Dawn)和黄昏(Dusk)样本,盐处理组与对照组各取2个时间点,共4组样本的叶片;
单细胞核测序:共获取17,994个高质量核,注释17个细胞簇,覆盖叶肉(海绵/栅栏)、表皮、保卫细胞、木质部、韧皮部等
① 景天酸代谢(Crassulacean acid metabolism, CAM)是C3光合作用二氧化碳固定途径的一个进化改良形式,大约有7%的陆生植物通过这种方式适应干旱环境。可诱导型CAM植物,例如冰叶日中花(Mesembryanthemum crystallinum,普通冰草),拥有一种独特的能力,能够在高盐度和水分不足的胁迫下从C3光合作用切换到CAM光合作用。
② 该研究通过单核RNA测序(snRNA-seq),结合一个全新高质量组装和注释的基因组,对冰草从C3到CAM的环境诱导转变进行了表征,以识别其潜在的调控因子。针对在黎明和黄昏采集的冰草叶片在C3和CAM切换过程中单核RNA测序数据的分析,揭示了在CAM诱导初期叶肉细胞中存在显著的转录变化。
③ 值得注意的是,该研究发现标明了黄昏时参与CAM或C3光合作用的不同叶肉亚细胞类型。细胞轨迹推断分析重建了全天候(24小时)的CAM和C3周期,直接比较了两条途径中的基因表达谱。这项对比研究揭示了CAM和C3细胞轨迹中关键昼夜节律基因的不同表达模式,表明昼夜节律调控与CAM的诱导之间存在联系。
图4-所有四个snRNAseq数据集的UMAP聚类
4.植物细胞类型特异性顺式调节元件的进化
 英文标题:Evolution of plant cell-type-specific?cis-regulatory elements发表期刊:bioRxiv
英文标题:Evolution of plant cell-type-specific?cis-regulatory elements发表期刊:bioRxiv
物种样本:核心物种:水稻(Oryza sativa,C3植物)
比较物种:玉米(Zea mays)、高粱(Sorghum bicolor)、黍(Panicum miliaceum)、Urochloa fusca
测序策略:单细胞ATAC测序、空间转录组学(Slide-Seq V2)、Iso-Seq全长转录组测序
DOI:https://doi.org/10.1101/2024.01.08.574753
发布时间:2024.01.08
取样策略:
单细胞ATAC测序:水稻:叶、根、种子、穗等9个器官;发育阶段:叶原基(P3-P6)、成熟叶(V4阶段);其他物种:玉米、高粱、黍、Browntop Signalgrass
空间转录组:水稻根
① Cis调控元件(Cis-regulatory elements, CREs)在基因表达调控中至关重要,但其进化机制的理解仍然具有挑战性。
② 该研究构建了一个全面的水稻(Oryza sativa)染色质可及性单细胞图谱,整合了来自103,911个细胞核、代表126种离散细胞状态的九个不同器官的数据。通过比较基因组学,分析了水稻与另外四种禾本科植物(玉米?Zea mays、高粱?Sorghum bicolor、黍?Panicum miliaceum?和?Urochloa fusca)中57,552个细胞核的细胞类型分辨染色质可及性之间的差异。
③ 研究发现,可及染色质区域(Accessible Chromatin Regions, ACRs)的保守性水平因细胞类型特异性程度的不同而有所区别。还发现ACRs、保守的非编码序列、细胞类型特异性、保守性和组织特异性切换之间存在复杂关系。此外,该研究发现表皮ACRs相比于其他细胞类型的ACRs保守性较低,这可能表明这些物种的L1来源的表皮层经历了更快速的调控进化。最后,研究人员鉴定并表征了一组与抑制性组蛋白修饰H3K27me3重叠的保守ACRs,这表明它们可能是由进化保留下来的类沉默子CREs。
④ 总体而言,这种比较基因组学方法揭示了植物细胞类型特异性CRE进化的动态特征。
图5-利用scATAC-seq数据鉴定水稻的细胞类型和表征ACRs
5.玉米叶原基单细胞转录组图谱揭示Kranz解剖结构调控机制
 英文标题:Single-cell?resolved?differentiation?of?pre-Kranz?anatomy?in?maize?leaf?primordia发表期刊:bioRxiv
英文标题:Single-cell?resolved?differentiation?of?pre-Kranz?anatomy?in?maize?leaf?primordia发表期刊:bioRxiv
物种样本:玉米(Zea mays?B73)、水稻(Oryza sativa Nipponbare)
测序策略:单细胞核转录组、bulk-RNA seq
DOI:https://doi.org/10.1101/2024.07.10.602848
发布时间:2024.07.14
取样策略:
从玉米叶原基:P3-P6原基分段取样(M3tip、M3middle、M3base;M2top、M2base)、3-4 mm P4原基单细胞核分离;水稻叶片原基:5 mm原基分段取样(R3tip、R3middle、R3base)
① 典型的C4植物如玉米,具有高度优化的Kranz型叶片结构,其中特定的花环状结构由围绕叶脉紧密排列的叶肉细胞和维管束鞘细胞组成。
② 该研究区分了早期叶原基中维管发育的活跃区域,并通过分段的玉米和水稻叶原基的比较转录组学分析,识别出可能参与早期Kranz发育的基因群。利用单细胞核RNA测序(snRNA-seq),进一步探讨了单个玉米叶原基中的细胞异质性和发育轨迹。借助原位杂交技术,识别了mGM和原形成层的细胞簇,候选标记基因显示出不同但相互关联的表达模式。维管标记基因ZmSHR1的定位先于ZmEREB161和ZmEREB114,这两者在原形成层的起始阶段表达。
③ 该研究描绘了从发展中的玉米原基尖端向下的潜在维管束鞘细胞亚群和不同层次的叶肉细胞。
④ 综上所述,该研究识别出潜在源自mGM或定位于原形成层的Kranz调控因子,并提供了在亚原基和单细胞分辨率下研究玉米和水稻叶脉发育的资源。
图6-玉米P4叶原基的细胞异质性
6.C4草本植物Kranz解剖结构形成过程中预存调控网络的重编程
 英文标题:Comparative spatiotemporal single cell transcriptomes reveal rewiring of pre-existing regulations during emergence of Kranz anatomy in C4?grasses发表期刊:bioRxiv
英文标题:Comparative spatiotemporal single cell transcriptomes reveal rewiring of pre-existing regulations during emergence of Kranz anatomy in C4?grasses发表期刊:bioRxiv
物种样本:玉米(Zea mays)、高粱(Sorghum bicolor)、狗尾草(Setaria viridis)、水稻(Oryza sativa)
测序策略:单细胞核转录组、高分辨率空间转录组
DOI:https://doi.org/10.1101/2024.10.28.620769
发布时间:2024.10.28
取样策略:
单细胞核&空间转录组:12日龄玉米幼苗基部茎段叶原基(P3-P6),通过Cellpose 2.0识别细胞壁轮廓,提取14,037个空间单细胞转录组
① 世界上许多高产的粮食作物和生物能源作物都采用C4光合作用,这种光合作用通过基于Kranz解剖结构的CO2浓缩机制实现了高光合效率。
② 该研究通过比较转录组学的方法,结合玉米(Zea mays)叶原基的单细胞空间转录组数据,以及三种C4植物(玉米、高粱、狗尾草)和一种C3植物(水稻)对应叶组织的单细胞RNA测序(scRNA-seq)图谱,研究了Kranz解剖结构发育和演化过程中涉及的调控网络。
③ 研究表明,Kranz解剖结构的形成涉及对现有调控模块的广泛招募和改造,特别是SHR-SCR模块和生长素信号通路。研究还发现,INDETERMINATE DOMAIN(IDD)家族转录因子(如IDD7和IDDP1)在这些模块的改造中发挥了重要作用。这种对现有基因调控程序的广泛招募和改造,是C4光合作用在演化过程中反复出现的基础机制。
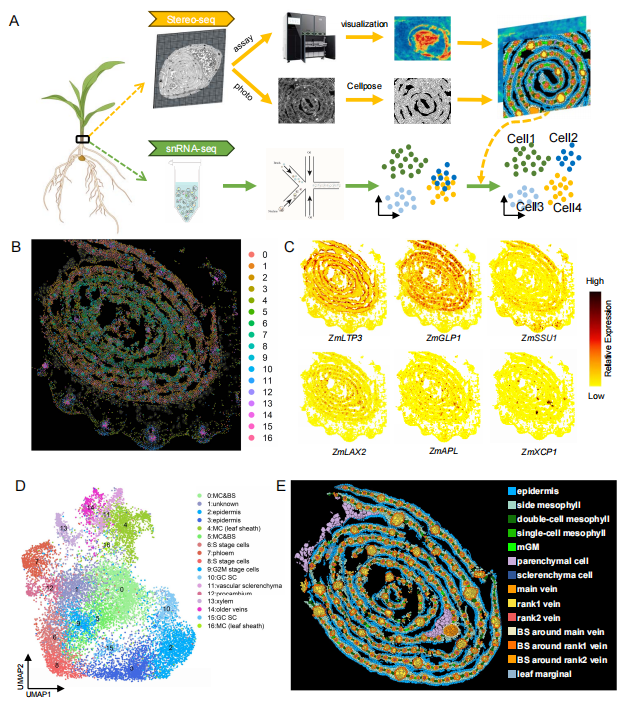
图7-玉米叶原基的空间转录组研究
7.C3-C4中间型十字花科植物维管束鞘细胞在光呼吸穿梭中的功能
 英文标题:Single-nuclei sequencing of Moricandia arvensis reveals bundle sheath cell function in the photorespiratory shuttle of?C3-C4?intermediate Brassicaceae发表期刊:bioRxiv
英文标题:Single-nuclei sequencing of Moricandia arvensis reveals bundle sheath cell function in the photorespiratory shuttle of?C3-C4?intermediate Brassicaceae发表期刊:bioRxiv
物种样本:C3-C4?中间型植物:堇娘芥(Moricandia arvensis)
测序策略:单细胞核转录组
DOI:https://doi.org/10.1101/2024.12.02.626447
发布时间:2024.12.02
取样策略:
单细胞核转录组:取5-6叶期堇娘芥幼苗的第五、第六叶片(距地面5mm处)
公共数据:拟南芥叶片单细胞测序数据
幼年期:0、1、2、3、4周;成年期:6、8、12周;老年期:6月、1年、2年。
① 基因表达的空间限制决定了细胞身份,并且是复杂植物性状的基础。在从C3光合作用向更高效的C4光合作用的进化过程中,将甘氨酸脱羧酶反应限制在维管束鞘细胞内,通过光呼吸甘氨酸穿梭启动了碳浓缩机制。通常认为,这一进化步骤在从祖先的C3光合作用向C4光合作用的过渡中起到了重要作用。执行这一穿梭机制的植物通常被称为C3-C4中间型植物或C2植物。在十字花科(Brassicaceae)家族中,这类植物至少独立进化了五次。然而,关于十字花科C3-C4中间型植物的生物化学研究仅限于少数关于叶肉细胞与维管束鞘细胞之间差异定位蛋白的案例研究。
② 该研究利用最近在单细胞转录组测序方面的进展,更好地理解新的细胞特化如何影响相互关联的途径。研究人员为具有C3-C4中间特征的堇娘芥(Moricandia arvensis)生成了单细胞核RNA测序数据集,并将其与公开可用的C3拟南芥(Arabidopsis thaliana)叶组织的单细胞转录组进行了比较,还通过免疫金标记技术结合电子显微镜独立验证了选定光呼吸蛋白的定位。
③ 该研究分析揭示了与光呼吸甘氨酸脱羧酶反应直接相关的基因表达的变化,同时也包括相关途径的基因表达转移,例如铵的同化、特定氨基酸的合成、氧化还原调节和对M. arvensis维管束鞘的转运。相比之下,在C4植物中,这些基因的表达并未局限于这一细胞类型。
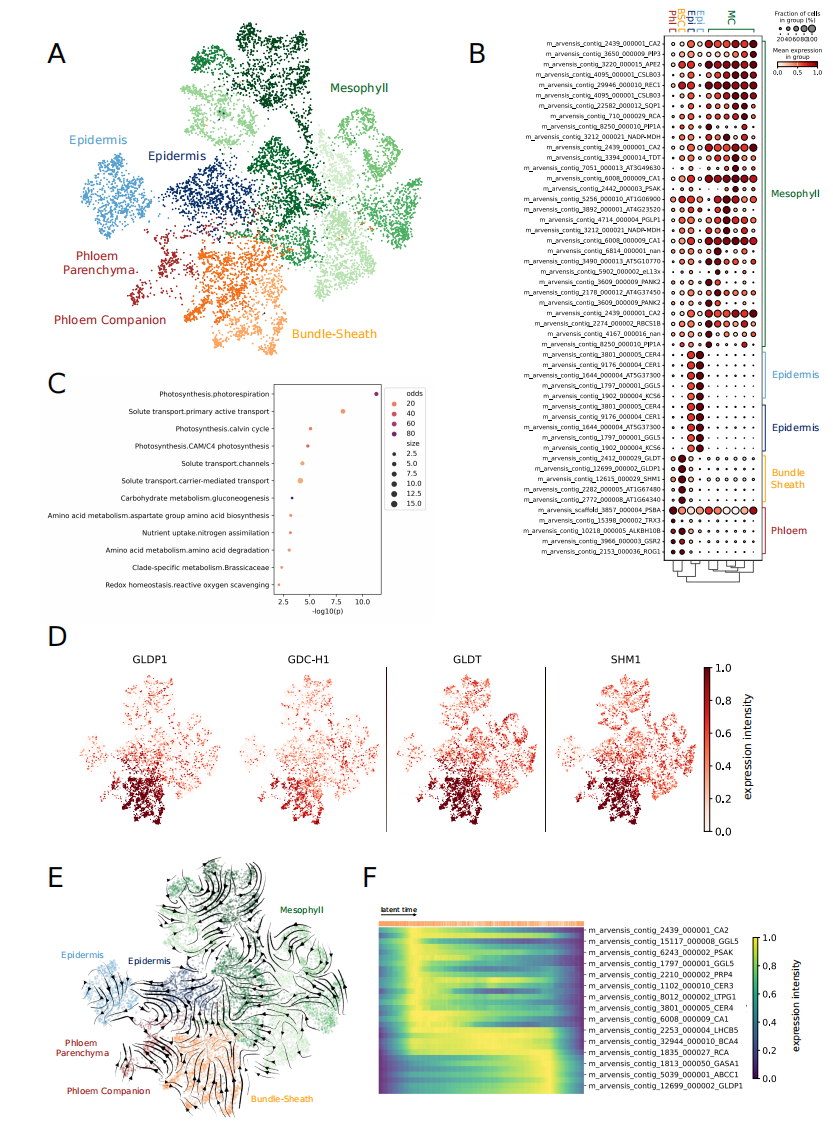
图8-堇娘芥叶片单细胞图谱
根据上述文献,可以总结出应用时空组学解析植物光合作用机制常用思路的技术路线图。